BIO – Medicina Costruzione Sociale nella Post-Modernità – Educational Papers • Anno V • Numero 20 • Dicembre 2016
Scritto in collaborazione con Eugenia D’Alterio – biologa
Introduzione
Nell’interpretazione evoluzionista, “la storia della vita” è scandita da transizioni evolutive [EVOLUTIONARY TRANSITION]1 che generano la nascita di nuovi livelli di organizzazione biologica e adattamento. Questi passaggi evolutivi comportano un’attività di selezione che agisce in ensemble sempre più complessi di entità biologiche. Le maggiori transizioni evolutive2 includono l’origine delle cellule procariote (con struttura cellulare semplice e materiale genetico libero nel citoplasma) e eucariote (cellule complesse con materiale genetico delimitato da membrana) e, successivamente, con la formazione di organismi pluricellulari e l’avvento dell’eusocialità (il livello più alto di organizzazione sociale che si realizza per alcune specie animali). Tutte, o quasi tutte, le forme di vita cellulari ospitano3 diversi elementi genetici “egoisti”, con vari livelli di autonomia, compresi plasmidi, trasposoni e virus. Questo articolo, seguendo i lavori di Eörs Szathmáry & John Maynard Smith, documenta che, almeno fino all’origine della multi-cellularità, le transizioni evolutive sono state guidate dalla co-evoluzione degli organismi che ospitarono [HOST] parassiti genetici, insieme alla condivisione di “beni”. I cosiddetti, “elementi genetici egoistici”, ipotesi del Selfish-DNA (DNA egoista), ipotesi che ha a vedere con le maggiori dimensioni del genoma4, hanno guidato le transizioni evolutive a due livelli distinti.
Primo livello: la modellazione matematica dei processi evolutivi, quali l’evoluzione delle popolazioni primitive di replicatori o di organismi unicellulari, indica che solo la crescente complessità organizzativa, ad esempio, l’emergenza di aggregati multicellulari, può avere impedito il crollo del sistema ospite-parassita, come l’endosimbiosi5, quando l’organizzazione risultava efficace. Secondo livello: l’analisi genomica comparativa rivela numerosi casi di reclutamento di geni con funzioni essenziali nelle forme di vita cellulare, inclusi quei geni che consentono le transizioni evolutive6. Ossia ogni individuo è una forma transazionale che apporta il suo contributo alla diversità biologica e quindi all’evoluzione delle specie.
Quindi, come proposta da Charles Darwin7 e consolidata nella neo sintesi darwiniana8, l’evoluzione9, in genere, procede, gradualmente, attraverso piccoli cambiamenti ereditabili (mutazioni genomiche, nel gergo moderno). Eppure è evidente che la diversità della vita sulla Terra, come la conosciamo oggi, deve essere stata modellata, in cima al cambiamento graduale, da numerose disordinate innovazioni che sembrano lasciare divari tra i diversi livelli di organizzazione biologica. Nei loro documenti e monografie seminali, Maynard Smith e Szathmáry10 hanno studiato tali transizioni evolutive innovative e hanno distinto tra transizioni maggiori e minori. Il termine “Transizione” non deve essere inteso nel senso che gli organismi, in un nuovo livello di complessità, sostituiscono quelli preesistenti, più semplici, ma piuttosto che i livelli più semplici e i livelli più complessi di organizzazione biologica vengono a convivere nella transizione. Nell’ultima versione del concetto11, Szathmáry elenca sette principali transizioni, dall’emergere di proto-cellule12all’avvento delle società umane con il linguaggio (tabella 1). Inoltre, molte transizioni minori possono essere delineate.
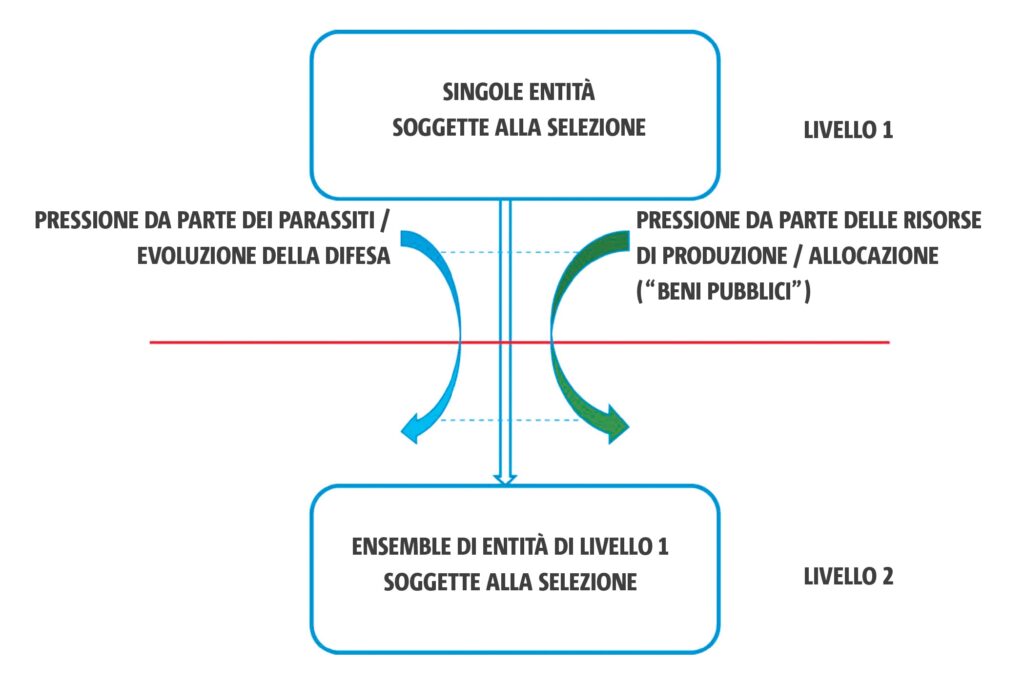
Le transizioni evolutive non sono arbitrariamente scelte, nemmeno nel caso di importanti innovazioni che si sono verificate nel corso della storia della vita. Szathmáry sottolinea due dimensioni di una transizione. La prima, acquisizione delle caratteristiche di ereditarietà, e la seconda, presenza di cooperatori dal momento che la vita ha cominciato13. Delle due, la seconda sembra essere quella più facile da descrivere in termini specifici e da definire con precisione per ogni singola transizione. Infatti, l’intuizione concettuale chiave di Maynard Smith e Szathmáry è che ciascuna delle transizioni comporta la nascita di una nuova, complessa entità selezionabile, in altre parole, un nuovo livello di selezione che agisce su insiemi di entità provenienti dal livello precedente (figura 1). L’origine degli organismi pluricellulari, che si è verificato in almeno tre occasioni indipendenti nel corso dell’evoluzione degli eucarioti, è, forse, il più evidente caso in cui la selezione a livello delle singole cellule è soppiantata dalla selezione sulle collettività cellulari. Si potrebbe sostenere che l’evoluzione dei sistemi complessi, in generale, comporta una transizione alla selezione a un livello superiore, quello di un insieme di entità, come, ad esempio, un gruppo di geni codificanti un particolare insieme di proteine, dalla selezione di entità singole (geni) da un livello più basso14. Così, il concetto di transizioni evolutive, in linea di principio, può essere percepito come una teoria generale dell’evoluzione della complessità15. In un piano di astrazione superiore, questo concetto è legato alla precedente teoria delle transizioni meta-sistemiche [MetaSystem Transitions], teoria definita come l’emergenza di meta-sistemi tramite l’integrazione di componenti originalmente indipendenti, che è stata sviluppato da Turchin nel 197016.
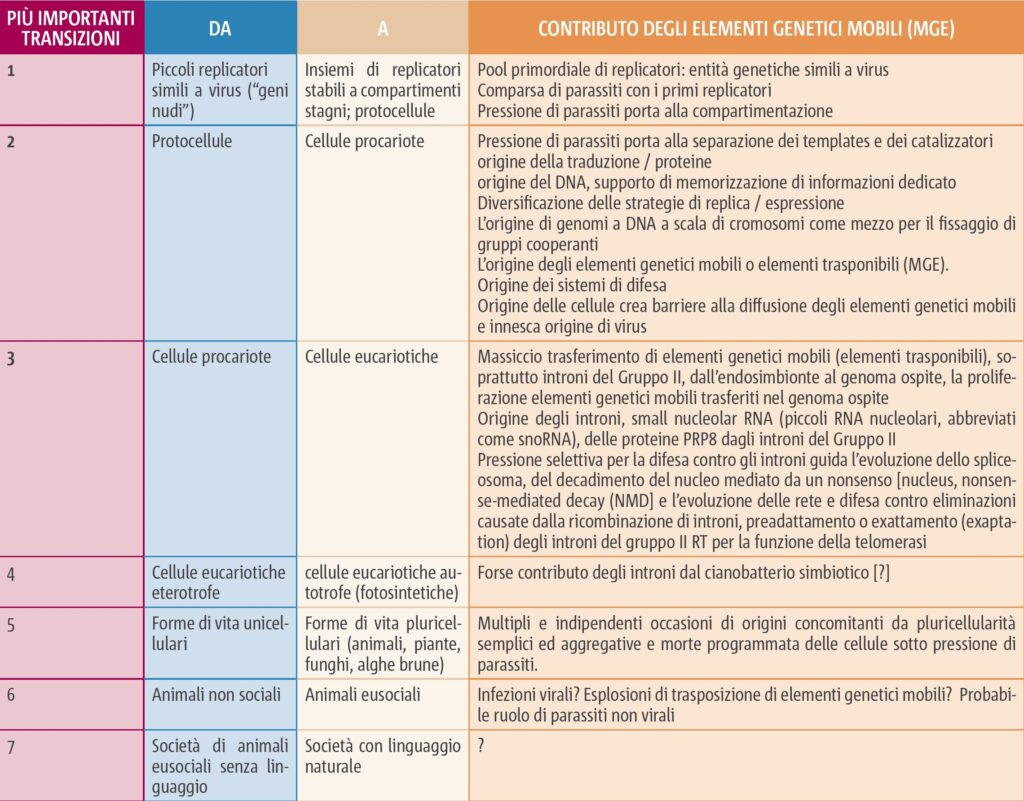
TABELLA 1. LE PIÙ IMPORTANTI TRANSIZIONI EVOLUTIVE E IL CONTRIBUTO DEGLI ELEMENTI GENETICI MOBILI (MGE – Mobile Genetic Elements)17 O ELEMENTI TRASPONIBILI
Ogni transizione importante sembra avere coinvolto l’evoluzione di meccanismi che controllano la selezione al livello precedente inferiore di organizzazione. Il ritorno al livello inferiore di selezione può essere dannoso per le entità complesse del livello superiore. I fattori evolutivi sottostanti le transizioni non sono ben compresi, in genere, anche se alcuni candidati forti, come l’endosimbiosi mitocondriale per l’origine degli eucarioti, sono evidenti.
Tutte o quasi tutte le forme di vita cellulare ospitano diversi parassiti genetici tra cui trasposoni (elementi genetici presenti nei genomi di procarioti ed eucarioti capaci di spostarsi da una posizione all’altra del genoma), plasmidi, virus e altri elementi genetici “egoistici”18. La co-evoluzione parassita-ospite è un importante aspetto di tutta l’evoluzione della vita19. In gran parte, questa co-evoluzione prende la forma della “corsa incessante agli armamenti”20 durante la quale gli ospiti cellulari evolvono multipli, in alcuni casi altamente elaborati, meccanismi di resistenza e di difesa, ai quali i parassiti rispondono evolvendo sistemi di contro-difesa21. Tuttavia, la cooperazione tra ospiti e parassiti integra la corsa evolutiva agli armamenti biologici. Ma gli elementi genetici parassitari possono fornire benefici per l’ospite proteggendolo da superinfezioni e, anche, attraverso preadattamento o exattamento [exaptation]22 del materiale genetico degli elementi egoistici per le funzioni dell’ospite23. Le sequenze derivate da elementi genetici mobili (MGE) costituiscono grandi frazioni dei genomi di molti eucarioti, ad esempio, fino al 90% di alcuni genomi vegetali e sono considerate essere importanti fattori propulsivi dell’evoluzione del genoma24. La mobilitazione degli Elementi Genetici Mobili [MGE] può essere utile per promuovere la diversificazione, specialmente sotto stress, ma può anche essere deleteria25. Un ruolo importante dei virus nella biologia dell’ospite è stato documentato anche nei procarioti come illustrato dalla trasduzione genetica26, in particolare il trasferimento dei geni fotosistema27 attraverso i cianofagi28, l’uso di profagi difettosi come veicoli per il trasferimento genico orizzontale (HGT), noti come agenti di trasferimento genico29 e, più in generale, attraverso l’assunzione di geni virali per le diverse funzioni dell’ospite30.
Le relazioni tra parassiti genomici e loro ospiti comprendono una vasta gamma di “egoismi”, cioè i parassiti formano un ampio spettro rispetto al costo sostenuto dall’ospite31. Ad una estremità dello spettro ci sono elementi benigni incapaci di replicazione autonoma e che replicano solo con il genoma ospite, in modo che il costo del parassita per l’organismo ospite è limitato al quasi trascurabile costo della sua replicazione. Al capo opposto ci sono i virus litici che replicano ad un numero estremamente elevato di copie e rapidamente uccidono l’ospite. Diversi elementi genetici egoisti, con vari gradi di autonomia, si trovano tra questi estremi, compresi virus temperati, trasposoni32 e plasmidi. Collegamenti evolutivi multipli (cioè geni condivisi) connettono elementi egoistici che differiscono in termini del costo per l’ospite quali virus litici e trasposoni33. Inoltre, lo stesso elemento spesso si alterna tra diversi stili di vita, per esempio, tra provirus34 a basso costo e virus litici ad alto costo, come nei casi accuratamente studiati di batteriofagi lisogeni35 e di retrovirus animali36, o tra un virus e un plasmide37. La maggior parte degli organismi cellulari ospitano in contemporanea diverse classi di elementi parassiti egoistici, con la conseguente conformazione di complessi ecosistemi di replicatori interagenti.
Numerosi studi ambientali indicano, con fiducia, che i virus sono le entità biologiche più abbondanti sulla Terra, con il numero di particelle virali in ambienti così diversi come l’acqua di mare, il suolo e gli intestini degli animali, superando il numero di cellule da uno a due ordini di grandezza38. Dato questo predominio dei virus nella biosfera, l’invariabile associazione di virus e/o altri elementi egoistici con forme di vita cellulare (incapsulati nel concetto di virocell39 di Forterre)40 e la comparsa di parassiti nei modelli teoretici e sperimentali di sistemi replicatori, un importante ruolo di questi elementi, in tutte le fasi della evoluzione della vita, appare evidente.
In questo articolo si cerca di documentare che gli elementi genetici egoisti rendono contributi fondamentali per le transizioni evolutive, almeno a due livelli. In primis, la corsa evolutiva agli armamenti parassita – ospite conduce a maggiore complessità organizzativa dei sistemi biologici, cioè serve come catalizzatore di transizioni evolutive. In secundis, virus ed elementi genetici mobili contribuiscono con geni specifici che svolgono ruoli importanti nella nascita di insiemi coerenti in un nuovo livello di complessità. Così, la co-evoluzione ospite-parassita sembra essere uno dei fattori trainanti chiave delle transizioni evolutive insieme con la condivisione di “beni pubblici” (allocazione delle risorse). La discussione che segue è limitata quasi esclusivamente alle prime grandi transizioni che coinvolgono le innovazioni a livello molecolare e livelli cellulari, con l’origine degli animali eusociali e l’origine della società umana, come livelli di organizzazione fuori dallo scopo del presente articolo.
I due livelli di grandi transizioni: dalle comunità pre-cellulari di replicatori a riproduttori protocellulari
Secondo Szathmáry41, la prima transizione importante nella storia della vita coinvolse l’origine delle proto-cellule, mentre la seconda transizione consistette nell’origine della traduzione e delle cellule procariote (tabella 1). La messa in scena di questi processi è meno evidente. Ad esempio, non è chiaro se la formazione dei cromosomi sia precedente (come ipotizzato da Szathmáry) o sia successiva all’origine della traduzione42. Pertanto, in questo articolo si trattano queste prime fasi di evoluzione come un’unica transizione complessa.
La presenza apparente di parassiti genomici, a tutti i livelli dell’organizzazione biologica e in associazione con tutte le forme di vita cellulari, suggerisce la possibilità che tali parassiti siano inerenti alla vita. In effetti, i parassiti emergono, costantemente, nei modelli teoretici dei sistemi semplici dei replicator43, come documentato da Szathmáry, Demeter, Koonin, Martin, Takeuchi & Hogeweg44. Senza entrare in dettagli matematici, è intuitivamente evidente che in qualsiasi sistema replicatore, che dipende da una risorsa che limita i tassi di replica, come ad esempio una replicasi45 (una polimerasi, enzima il cui ruolo è associato alla polimerizzazione degli acidi nucleici) emergono “imbroglioni”46 che sfruttano la risorsa senza produrla47. Infatti, si può prevedere che la fase finale nell’evoluzione degli “imbroglioni” sia un genoma minimale costituito esclusivamente da segnali per il riconoscimento e l’utilizzo dei replicasi. Che questo risultato sia realistico in un sistema replicatore semplice è indicato dai risultati dei primi esperimenti classici “in vitro darwiniani” di Spiegelman e collaboratori48 (successivamente ripetuti con varie modifiche in diversi laboratori) nei quali la genomica a RNA di batteriofago Qb è stata incubata con la fago replicasi per un tempo limitato. Dopo trasferimenti multipli seriali tra provette, la popolazione era stata trovata consistere di un mini genoma che aveva perso tutti i geni codificanti proteine e mantenuto solo i segnali per l’interazione con le replicasi49.
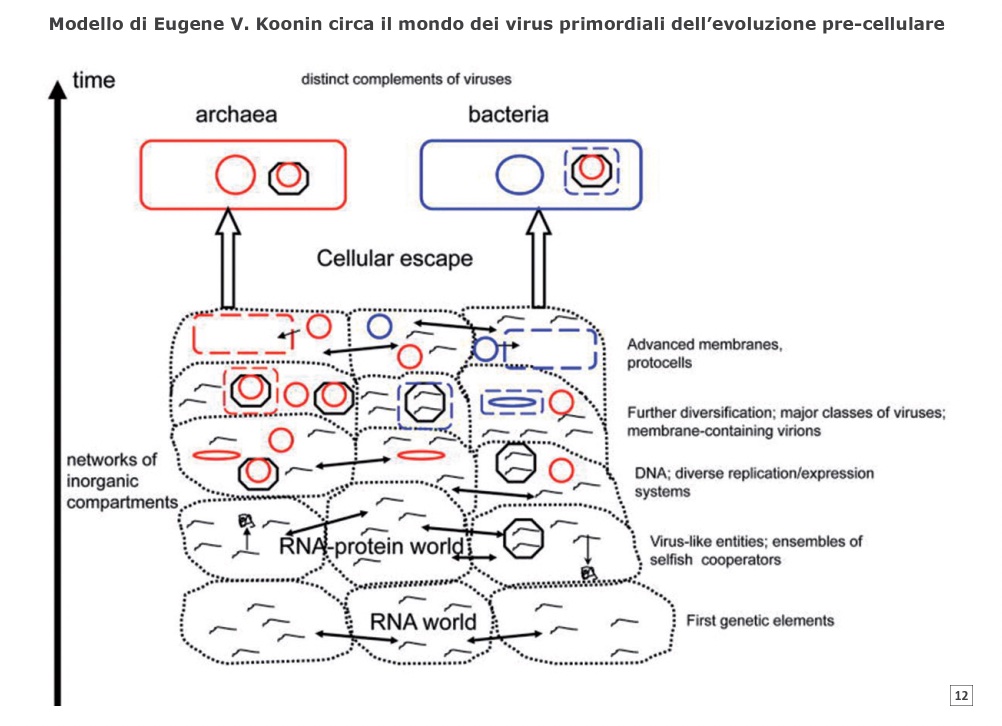
La fase pre-cellulare dell’evoluzione biologica (quando ci si riferisce ad una fase pre-cellulare, non si intende accennare ad una mancanza di compartimentazione, piuttosto solo alla mancanza dell’organizzazione tipica delle cellule moderne) può essere plausibilmente immaginata come simile ad uno stato virale. In un tale modello, i soggetti di evoluzione (cioè, selezione e deriva casuale) erano piccoli elementi genetici nella gamma di dimensioni dei virus a RNA esistenti, vale a dire 1-30 kb circa, che erano parzialmente o completamente egoisti50. La tesi sostenuta da Dawkins, biologo inglese, nel suo libro “Il gene egoista”, è che i geni che vengono trasmessi sono solamente quelli le cui conseguenze servono per i loro stessi interessi (continuare ad essere replicati), non necessariamente quelli dell’organismo né tanto meno quelli di un livello ancora più grande, ossia il vantaggio va ai singoli geni piuttosto che all’individuo e/o specie. (tabella 1). Dato che cellule complesse non si erano ancora sviluppate, è, probabilmente, inopportuno parlare di virus rispetto a questo stadio dell’evoluzione, ma sembra innegabile che la vita cellulare, di tipo moderno, fu preceduta da pool di elementi genetici che erano simili a virus in termini di dimensioni, caratteristiche e parziale autonomia51. Indipendentemente dai dettagli molecolari, la differenziazione in cooperatori e imbroglioni emerse già al momento della comparsa di pool genetici primordiali.
Un’intuizione teorica straordinaria è che una popolazione di replicatori, spazialmente omogenea, è incline ad essere sorpassata da parassiti “imbroglioni” e per questo è, generalmente, destinata a crollare52. L’unica strada per la stabilità per una popolazione di replicatori di fronte all’assalto parassita sembra essere la compartimentazione: i parassiti possono essere eliminati da una popolazione, o almeno tenuti sotto controllo53. La compartimentazione crea barriere per la diffusione di parassiti e condizioni per la cooperazione tra replicatori non-parassitari che può risultare in un insieme dei collaboratori che supera i parassiti a livello locale e che stabilizza il sistema in co-evoluzione a livello globale54. Così, i parassiti promuovono la selezione di gruppo tra collaboratori, aprendo la strada per la transizione evolutiva55. Pertanto, negli insiemi pre-cellulari di elementi genetici simili a virus, ci sarebbe selezione per aumentare la dimensione del genoma, unendo segmenti come mezzo di fissaggio di combinazioni di geni vincenti. In un sistema compartimentalizzato, la co-evoluzione di ospiti e parassiti si traduce, inevitabilmente, nell’inizio di una corsa evolutiva degli armamenti, uno dei principali fattori in tutta l’evoluzione biologica, che porta ad un ulteriore aumento della complessità di entrambi, ospiti e parassiti, in particolare attraverso l’evoluzione di sistemi di difesa e contro-difesa. Difesa e contro-difesa, più probabilmente, sono tra le prime funzioni pre-biologiche.
Per quanto riguarda le specifiche forme di compartimentazione, i micro-ambienti protettivi, come le vescicole di membrana simili a quelle emesse da alcuni archeobatteri e batteri moderni, ma inizialmente con membrane abiogeniche, potrebbe anche aver contribuito alla compartimentazione, interazione e co-evoluzione di elementi nei pool genetici primordiali.56 Inoltre, anche se il pensiero convenzionale colloca l’origine dei virioni (e in buona fede, quindi, dei virus) dopo l’avvento delle cellule, esiste la possibilità che semplici virioni (capsids: il virione è racchiuso da un involucro proteico chiamato capside) precedano le cellule, essendosi evoluti come mezzi di protezione e di diffusione di elementi genetici primordiali.57 Nella scala evolutiva il virione( particella virale) precede il virus, al di sotto del virione ci sta il virino e, più in basso di esso, il viroide ed il prione. Un virione, infettando una singola cellula ospite, è in grado di produrre migliaia di discendenti utilizzando i meccanismi di replicazione del DNA, trascrizione e traduzione della cellula infettata. Questa moltiplicazione virale è spesso sufficiente a uccidere la cellula ospite rompendola (lisandola).
Allo stato attuale, l’ipotesi del mondo a RNA58 sembra essere l’unico modello plausibile per la transizione da prebiotico all’evoluzione biologica.59 Nel mondo a RNA, tutte le reazioni, compresa la replicazione dei genoma ad RNA, sono considerate essere state catalizzate da ribozimi. Dato che i parassiti sono inerenti ai sistemi di replicatori, i parassiti devono essere apparsi già nel mondo a RNA portando alla compartimentazione e complessificazione cellulare come suggerito sopra. Modelli matematici circa l’evoluzione del sistema replicatore60 suggeriscono che la resilienza61 ai parassiti aumenta quando la conservazione dell’informazione e le funzioni catalitiche sono separate, cioè con l’avvento di dispositivi operativi dedicati (specializzati), come le proteine e i vettori di informazione dedicati, quale il DNA.62 A livello intuitivo, i sistemi con separazione delle funzioni informative e operative e con vettori di informazione dedicati sarebbero più resistenti ai parassiti rispetto ai sistemi senza questa separazione perché i parassiti possono solo prendere in consegna la componente operativa ma non la componente informativa, così i sistemi operativi dedicati aumentano la possibilità che la cellula ospite sopravviva all’invasione. Così, l’origine della traduzione (anche se decifrare uno scenario concreto in questo caso incontra grande difficoltà63 e l’origine dei genomi a DNA, almeno in parte, sono stati guidati dalla corsa agli armamenti ospite-parassita. La traduzione potrebbe emergere solo in un insieme di collaboratori, data la necessità di più componenti.64 L’avvento della traduzione in tal modo ha dato un vantaggio immediato, sotto forma di catalizzatori altamente efficienti, agli ospiti in gara con i parassiti. Tuttavia, il passo successivo nella corsa sarebbe stato l’adattamento dei parassiti al nuovo mondo, cioè l’evoluzione della capacità di dirottare proteine prodotte dall’ospite per essere impiegate nella replica dei parassiti stessi, come le polimerasi. Gli organismi ospiti risposero sviluppando (evolvendo) specificità enzimatica e compartimentalizzazione (replica del genoma ospite catalizzato in cis65) per escludere i parassiti e, in risposta, alcuni dei parassiti catturarono geni codificatori di proteine che potevano beneficiare la replicazione del parassita, utilizzando il macchinario di traduzione dell’ospite per produrre le proprie proteine.
Il pool genetico primordiale, molto probabilmente si è evoluto dalla sola fase RNA (mondo a RNA) verso una miscela di elementi genetici con tutte le strategie di replica impiegate da elementi egoistici esistenti56. Per motivi chimici, la comparsa del DNA è un pre-requisito dell’evoluzione di genomi più grandi e complessi che alla fine raggiunsero la dimensione del cromosoma, ulteriormente accrescendo la propria complessità e preparando il terreno per la comparsa di cellule di tipo moderno. La corsa agli armamenti tra i parassiti e gli ospiti, in sé, potrebbe esser stata una forza trainante, dietro l’origine del DNA, come una forma di resistenza del genoma per difendere i meccanismi evoluti dall’ospite contro i parassiti a RNA57.
Il DNA non avrebbe potuto emergere dal mondo ad RNA senza la trascrizione58 inversa59. I retro-elementi, gli elementi egoistici più comuni negli eucarioti60 moderni, ampiamente rappresentati anche nei batteri e in alcuni archeobatteri (anche se meno abbondanti che negli eucarioti), devono essere stati tra le prime classi di elementi che si sono evolute nel pool genetico primordiale dopo l’avvento della traduzione61. L’integrazione di tali elementi nei genomi ospiti deve essersi co-evoluta con l’aumento delle dimensioni dei genomi a DNA, stabilendo una delle tendenze dominanti della co-evoluzione ospite-parassita. Elementi trasponibili con genomi a DNA, molto probabilmente, si sono evoluti nella stessa fase. L’integrazione genomica beneficiò i parassiti fornendo loro una strategia evolutiva di diversificazione del rischio [bet hedging]62, vale a dire la capacità di alternare propagazione passiva all’interno dei genomi ospiti con riproduzione autonoma63. Tuttavia, gli organismi ospiti potrebbero, anche, aver estratto benefici da questo fenomeno attraverso il reclutamento di elementi egoistici, o di loro parti, per le funzioni di accoglienza. Questa strategia evolutiva probabilmente precede le cellule di tipo moderno e ha giocato un ruolo importante nella transizione evolutiva.
Sono stati proposti scenari evolutivi in cui i genomi a DNA, originariamente, evolsero in virus e, successivamente, presero il sistema genetico di proto-cellule basate sull’ RNA64. Come sottolineato in precedenza, l’origine del DNA in elementi egoistici è plausibile nel contesto della corsa agli armamenti nel pool genico65 primordiale. Tuttavia, l’esistenza di cellule basate unicamente in RNA sembra incontrare notevoli difficoltà, il che mette queste ipotesi in discussione. Uno scenario più misurato, comprende genomi a DNA già in una fase iniziale dell’evoluzione delle cellule.
La comparsa di cellule di tipo moderno, con membrane impermeabili ai polimeri, comportò una nuova barriera, ripida, alla diffusione di parassiti che da allora in poi avevano bisogno sia di diffondersi attraverso percorsi generali di Trasferimento di Geni Orizzontale (HGT)66, sia di evolvere dispositivi speciali, come virioni, per sopravvivere fuori delle cellule ospiti e infettarne nuove. Così, l’avvento di forme di vita cellulare di tipo moderno causò la differenziazione di elementi egoistici in un continuum di forme che differiscono rispetto al costo per l’ospite e alla trasmissività67. Così, da considerare che ad un’estremità ci sono elementi a basso costo e bassa trasmissività, come plasmidi a basso numero di copie, mentre nell’altra estremità ci sono virus che uccidono l’ospite e si trasmettono ad un nuova cellula con alta efficienza.
Così, senza dubbio, nelle prime due più importanti transizioni evolutive nell’evoluzione della vita, la co-evoluzione, parassiti genetici con i loro ospiti, causò una eccezionale complessificazione su entrambi gli aspetti della questione ospite-parassita.
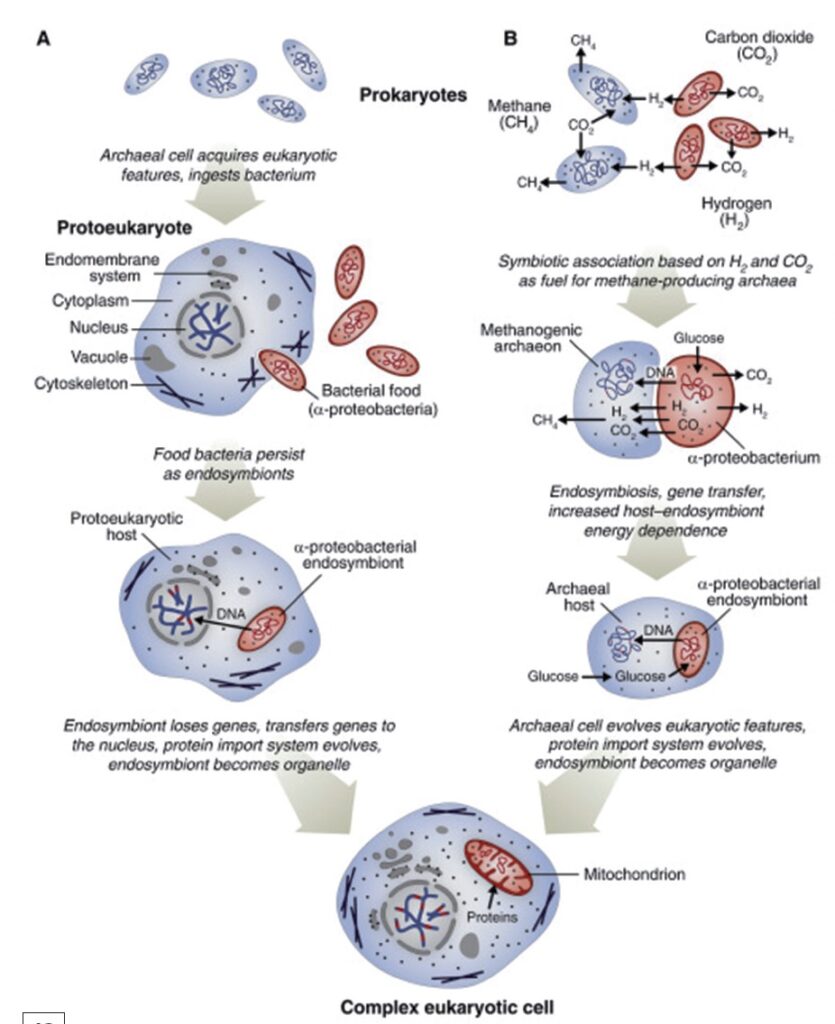
Il terzo passaggio: l’origine delle cellule eucariote
Dopo l’origine delle cellule, la comparsa di cellule eucariote (Eukaryogenesis) coinvolse, probabilmente, il più grande salto in complessità che mai sia avvenuto nel corso dell’evoluzione della vita68. Infatti, una tipica cellula eucariotica è circa 1000 volte più grande, in volume, di una tipica cellula archea o batterica69, e contiene un sistema end membranoso comprendente organelli70 limitati da membrane come i mitocondri e il nucleo e viene accuratamente compartimentalizzata in modo che la libera diffusione dei bio-polimeri è fortemente limitata71. Questo accentuato salire nella complessità organizzativa della cellula è accompagnato da una maggiore complessità genomica72. Gli eucarioti mancano dell’accoppiamento stretto tra la dimensione del genoma e il numero di geni codificanti proteine, cosa che caratterizza i procarioti che hanno un genoma molto più piccolo rispetto agli eucarioti che hanno, in genere, genomi molto più grandi73. In alcuni animali e piante, questa mancata corrispondenza raggiunge proporzioni grottesche in modo tale che le sequenze codificanti proteine rappresentano solo il 1-2% del genoma74. Ancora più importante, gli eucarioti differiscono dai procarioti nel principio fondamentale dell’architettura dei geni: i geni degli eucarioti sono interrotti da multiple sequenze non codificanti, gli introni75. Gli introni76, non codificanti, sono rimossi dalle trascrizioni primarie dei geni eucariotici mentre le sequenze codificanti d’accompagnamento, gli esoni, rimangono77, processi collegati da un meccanismo molecolare molto complesso, lo spliceosoma78. Sebbene la maggior parte dei genomi eucarioti unicellulari sono poveri di introni, le ricostruzioni evoluzionistiche indicano che l’ultimo antenato comune degli eucarioti esistenti era ricco in introni, con 6-7 introni per gene, prossimo alla densità di introni nei vertebrati moderni79. La struttura esone-introne dei geni codificanti proteine dà un importante contributo alla complessità dei proteomi80 eucarioti attraverso lo splicing alternativo81 che produce multipli di proteine isoforme (l’mRNA media la possibilità da parte di un gene di produrre isoforme differenti di una stessa proteina). Su un piano diverso, l’architettura esone-introne dei geni eucariotici sembra essere legata alla complessità organizzativa delle cellule eucariotiche. Lo splicing82 è strettamente connesso con l’esportazione nucleo – citoplasmatica di mRNA maturo e l’origine del nucleo stesso avrebbe potuto essere guidata dalla necessità di impedire l’accesso ai citoplasma immaturo di, eventuali, trascrizioni di introni che sarebbero stati tradotti per produrre proteine aberranti, spesso proteine tossiche, con catastrofiche conseguenze per la cellula83.
Tutti gli eucarioti esistenti possiedono mitocondri o loro derivati e in scenari di endosimbiosi circa l’origine degli eucarioti stessi84. La transizione procarioti – eucarioti sembra essere stata spinta proprio dall’endosimbiosi tra un a-proteobacterium85, il futuro mitocondrio e una cellula ospite che molto probabilmente era un archea del gruppo Lokiarchaeota86, come sostenuto da Spang, Embley, Williams & Koonin87. Ma la natura del proto-mitocondrio rimane oggetto di dibattito, con argomenti presentati a favore dell’evoluzione delle cellule eucariote primitive prima dell’endosimbiosi88. Le difficoltà incontrate da questi scenari evolutivi riguardo i “proto-eucarioti” sono duplici: in primo luogo, eucarioti a-mitocondriali non sono stati scoperti, nonostante notevoli sforzi di ricerca e così si è costretti a ipotizzare che si siano estinti; in secondo luogo, in questi scenari, non sembra esserci alcuna plausibile catena causale per l’origine delle complesse caratteristiche dell’organizzazione cellulare degli eucarioti. Anche se il dibattito sull’origine degli eucarioti certamente non è finito, il resto della presente discussione si atterrà alla teoria endosimbiontica.
L’addomesticamento del proto-mitocondrio, apparentemente, innescò una valanga di eventi che, in tappe, apparentemente rapide, nella scala evolutiva, condussero alla transizione (passaggio da una situazione ad un’altra)89. Sembra probabile che l’innesco primario della trasformazione della organizzazione cellulare durante la genesi degli eucarioti fu il forte impulso alla produzione di energia fornita loro dai proto – mitocondri alla cellula chimerica (cellula eucariote)90. L’aumento di produzione di energia determinerebbe la crescita del volume cellulare concomitante con un calo della dimensione della popolazione effettiva con la conseguente riduzione della potenza di selezione91. In queste condizioni, pure piccole o moderate mutazioni deleterie si sono fissate attraverso la deriva genetica92. Nella evoluzione della cosiddetta cellula chimerica, un processo dominante fu l’integrazione di un endosimbionte a DNA nel genoma ospite, sostenuta dalla costante lisi dei simbionti. A quanto pare, questo flusso unidirezionale di DNA coinvolse una vasta proliferazione di introni gruppo II, retro-elementi batterici che invasero i geni dell’organismo ospitante in gran numero e diedero origine sia agli introni dello spliceosoma che alle porzioni di RNA attivi dello spliceosoma stesso94, è anche un derivato dagli introni del Gruppo II, un inattivato trascrittasi inversa (RT)95. In questo scenario, l’origine dello spliceosoma e del nucleo, con i suoi elaborati complessi di pori che connettano lo splicing con l’esportazione di mRNA, rappresenta, in modo efficace, l’evoluzione della difesa contro deleteri effetti degli Elementi Genetici Mobili (MGE)96 L’evoluzione di alcuni altri grandi sistemi funzionali della cellula eucariotica, come il decadimento mediato da mutazioni nonsenso97 e la rete di segnalazione dell’ubiquitina,98 possono, anche, essere considerati nel contesto di aggiunte di ulteriori livelli di difesa99.
È importante sottolineare che, nel caso della eukaryogenesis, l’invasione di MGE (introni del Gruppo II all’origine dello spliceosoma degli introni), apparentemente, diede un duplice contributo alla complessità della cellula eucariotica: primariamente, innescando l’evoluzione di molteplici linee elaborate di difesa e, secondariamente, permettendo lo splicing alternativo100. Tuttavia, il contributo dei retro-elementi batterici alla eukaryogenesis non si limita a questi due effetti importanti ma, inoltre, include la linearizzazione dei cromosomi101. Il passaggio da circolare a cromosomi lineari sembra essere stata una condizione necessaria per impedire la devastante instabilità del genoma che sarebbe stata causata dalla ricombinazione tra le copie di introni all’interno di un genoma circolare102. La replica dei cromosomi lineari richiede la copia di ripetizioni terminali che è catalizzata dalla sub-unità RT della telomerasi103, derivata da RT codificata dallo stesso Gruppo II di introni, che furono gli antenati degli introni spliceosomali e i componenti chiave dello spliceosoma (grossa particella ribonucleoproteica in cui avviene il processo di splicing del pre-mRNA, RNA messaggero immaturo) stesso104. Lo splicing, ricordiamo, è una modifica del nascente pre-mRNA che avviene insieme o dopo la trascrizione, nella quale gli introni sono rimossi e gli esoni vengono uniti.
Anche per l’evoluzione dei mitocondri, le loro caratteristiche morfo-chimiche suggeriscono una origine endo-simbiontica, ossia che in origine fossero batteri aerobi indipendenti poi integratisi in una cellula ospite105.
La grande maggioranza degli eucarioti si riproduce sessualmente e la presenza di geni meiotici dedicati nel genoma di forme anche apparentemente asessuate implica che la meiosi106 e il sesso sono caratteristiche ancestrali degli eucarioti. Quindi, l’origine del sesso (meiotico) dovrebbe essere considerato parte integrante del passaggio importante che condusse all’origine degli eucarioti stessi. L’origine e conservazione della meiosi e del sesso sono stati oggetto di un’ampia analisi teorica107. La causa principale della quasi ubiquità del sesso negli eucarioti sembra essere quella di evitare, attraverso una regolare ricombinazione meiotica, ciò che nella biologia evoluzionista viene chiamato come il Muller’s rachet (o ingranaggio di Muller)108, cioè l’accumulo di mutazioni deleterie in una popolazione clonale che conduca ad eventuali mutational meltdown109 [fusione di mutazione]110. Questo particolare meccanismo di ricombinazione avrebbe potuto diventare una necessità una volta che il trasferimento orizzontale di geni, che esegue la stessa funzione nei procarioti111, fu ridotto dall’evoluzione della compartimentalizzazione intracellulare degli eucarioti. La generazione di diversità potrebbe essere un ulteriore vantaggio del sesso112. Tuttavia, questi vantaggi spiegano facilmente il mantenimento ma non l’origine del sesso. Pertanto, è stato proposto che il sesso, originariamente, si evolse non perché avvantaggiasse i rispettivi organismi, ma sotto la pressione dei MGE (ricordiamo che in genetica, si definiscono MGE quei elementi genetici mobili e trasponibili nel genoma, in inglese MGE: Mobile Genetic Elements), la cui diffusione è promossa dalla ricombinazione meiotica113. Anche se questo rimane un ipotetico meccanismo, il ruolo dei MGE nell’evoluzione della meiosi è compatibile con l’osservazione che gli omologhi archeali degli enzimi chiave della meiotica a doppio filamento, quali la nucleasi Mre11114 e la ATPasi recombinogenic Rad50 –meccanismi di riparazione che fanno parte del complesso MRN, interrompono la riparazione115 e formano operoni116 che spesso si trovano su plasmidi o resti di plasmidi integrati nel cromosoma117. In teoria, nella fase iniziale della evoluzione degli eucarioti, quando la diffusione di plasmidi mediante trasferimento orizzontale era ostacolata, la selezione favorì varianti altamente ricombinogeniche di queste riparazioni geniche, che ha promosso la nascita di meiosi e con essa la sua diffusione. Questo scenario, anche se speculativo, mette in evidenza un netto e potenzialmente importante ruolo dei MGE nelle transizioni evolutive. In questo caso, oltre al reclutamento dei geni dei MGE per una funzione molecolare al nuovo livello, una componente importante della transizione avrebbe potuto essere spinta dagli “interessi egoistici” dei MGEs.
Così, elementi genetici “egoisti” sono stati uno dei fattori chiave nel maggior passaggio evolutivo [transizione evolutiva] associato con la nascita degli eucarioti a cui hanno contribuito sia attraverso la corsa agli armamenti, che ha causato l’evoluzione dei sistemi di difesa complessi, e sia attraverso la donazione diretta di parti essenziali del macchinario cellulare eucariotico.
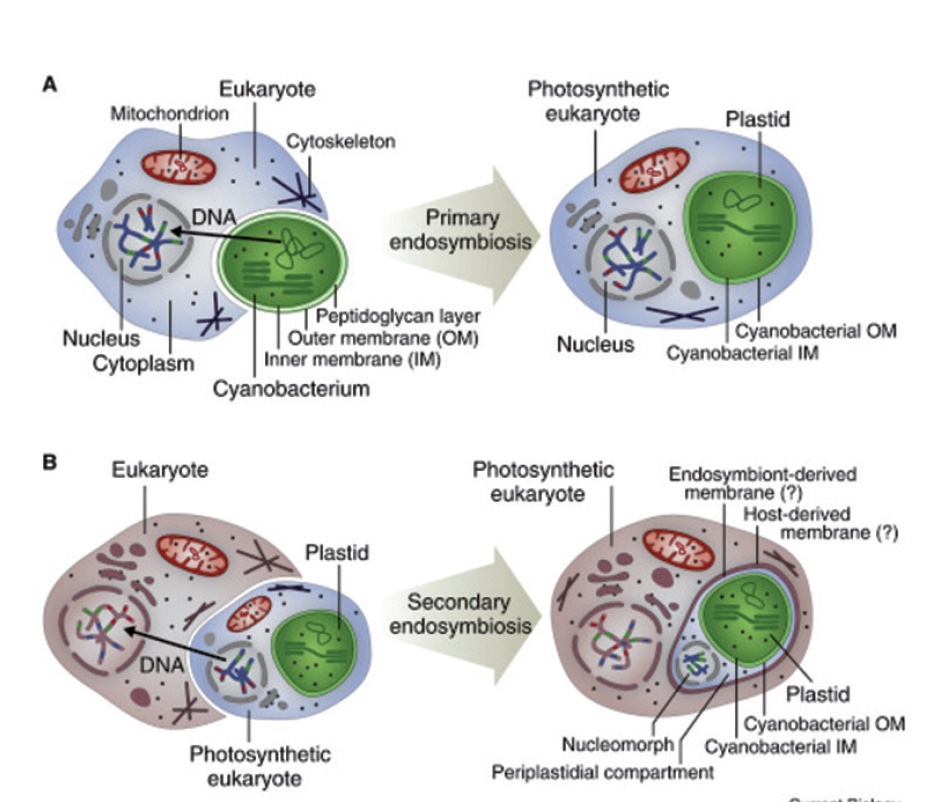
Il successivo passaggio: l’origine della pluricellularità
In questa argomentazione saltiamo il quarto passaggio nella lista di Szathmáry118, l’acquisizione dei cianobatteri119 endosimbionti120 che diventarono i cloroplasti nell’antenato comune di piante e alghe. Il passaggio successivo importante è l’evoluzione della multi cellularità. Sorprendentemente, a differenza delle transizioni precedenti, l’origine delle cellule primordiali e l’eukaryogenesis, la pluricellularità non è una caratteristica unica ma, piuttosto, si è evoluta in modo indipendente in più occasioni (quindi, in realtà si tratta di una serie di transizioni simili)121. Alcune di queste coinvolgono l’emergere di complesse forme di vita multicellulare, con cellule marcate [marked cell] e la differenziazione dei tessuti, vale a dire animali, piante, funghi e alghe brune. Oltre a queste forme avanzate, le versioni ancestrali più semplici di pluri-cellularità, con un certo livello di differenziazione cellulare, si evolse anche negli eucarioti tradizionalmente considerati unicellulari122, e in alcuni gruppi di procarioti, come i cianobatteri, gli attinomiceti123 e i mixobacteria124. Inoltre, molti batteri e archaea hanno la capacità di auto-organizzarsi in aggregati multicellulari, in particolare, attraverso quorum sensing125 come postulano Miller, Bassler, Boyer & Wisniewski-Dyé126. Il grado di specializzazione delle cellule, se presenti, in tali formazioni multicellulari transitorie, non è ben compreso.
Una delle caratteristiche delle forme di vita pluricellulari è la morte cellulare programmata127. I sistemi di morte cellulare programmata funzionano in difesa contro gli agenti patogeni e controllano la proliferazione cellulare così come alcune fasi di sviluppo normale128. Negli organismi multicellulari, la morte cellulare programmata appare “naturale”, un meccanismo che controlla un livello organizzativo inferiore, singole cellule, a beneficio del livello superiore, l’organismo, uccidendo le cellule che diventano più nocive che utili per l’organismo stesso. Però, numerose linee indipendenti di prove segnalano l’esistenza di morte cellulare programmata anche in molte, probabilmente la maggior parte, forme di vita unicellulari, cosa che, a prima vista, appare paradossale129. In effetti, negli organismi multicellulari, la morte cellulare programmata è “altruista” con rispetto alle singole cellule: alcune cellule si suicidano in modo che altre cellule dello stesso organismo (e quindi l’organismo nella sua interezza) possano vivere. Questo principio non può funzionare in forme unicellulari di vita; tratti altruistici possono evolvere solo quando vi è selezione a livello di gruppi di cellule, cioè al momento di transizione verso la pluricellularità. Le forze trainanti dietro tale transizione non sono evidenti perché in genere il tasso di riproduzione è il più alto in uno stato di cellula libera (ad esempio, nell’inibizione da contatto130 durante la crescita in coltura cellulare). Tuttavia, la situazione cambia quando le cellule sono soggette a pressioni da agenti patogeni. In questo caso, il suicidio di cellule infette può proteggere le cellule vicine in un aggregato multicellulare e, quindi, può essere vantaggioso per l’aggregato come un tutto. La ricerca delle fasi dello spazio di un modello matematico, basato sull’agente della co-evoluzione ospite – parassita, ha dimostrato che l’aumento della pressione parassita, infatti, conduce ad un aumento a vantaggio degli aggregati cellulari dotati di un meccanismo di morte cellulare programmata e, ad una certa soglia della pressione, questa strategia diventa l’unica sostenibile131. La conclusione principale di questo studio di modellazione è che la pluricellularità e la morte cellulare programmata sono inestricabilmente abbinate: l’una non si può evolvere senza l’altra. Come in qualsiasi comportamento altruistico, l’evoluzione della morte cellulare programmata è ostacolata da “imbroglioni”132, in questo caso, cellule che scaricano i macchinari suicidi ma che beneficiano del suicidio di altre cellule; la proliferazione di “imbroglioni” può portare al collasso dell’intero aggregato. La minaccia rappresentata dagli “imbroglioni” può essere superata tramite la selezione di parentela (inclusive fitness), per cui le cellule microbiche che formano un aggregato multicellulare sono parenti stretti in modo che il suicidio altruistico promuove, in modo efficace, la sopravvivenza del genotipo delle cellule morenti133. La selezione di parentela è probabile che sia stato il meccanismo essenziale nell’evoluzione della multicellularità nella difesa da patogeni.
Data l’ubiquità della morte cellulare programmata, in particolare sotto forma dei sistemi procariotici tossina-antitossina (TA)134, sembra probabile che questo fenomeno si è evoluto in concomitanza con, o almeno subito dopo, la formazione delle prime cellule. Di conseguenza, semplici forme di pluricellularità, aggregazioni di cellule con poca o nessuna differenziazione, sono, molto probabilmente (o quasi), tanto vecchie come la vita cellulare stessa. L’accoppiamento evolutivo della morte cellulare programmata con la multicellularità presenta l’aspetto del paradosso dell’uovo o la gallina: la morte cellulare programmata non può evolversi senza la multicellularità e la pluricellularità non sembra essere evolutiva in assenza del guadagno in fitness fornito dalla morte cellulare programmata [PCD] sotto la pressione di parassiti. La soluzione è suggerita dalle proprietà dei sistemi TA [tossina-antitossina]135, che sono in parte elementi genetici egoisti che creano dipendenza per le cellule che li ospitano136, come si cercherà di illustrare a seguito. I sistemi di TA [tossina-antitossina] potrebbero essersi evoluti come moduli di plasmidi di dipendenza in organismi unicellulari e poi reclutati dall’aggregazione di microbi come dispositivi di morte cellulare programmata preconfezionati137.
Così, la corsa agli armamenti ospite-patogeno probabilmente è stato uno dei i fattori chiave che stanno dietro l’evoluzione della semplice pluricellularità, che preparò il terreno per la nascita di avanzati organismi multicellulari, in diverse occasioni indipendenti. Sembra probabile che l’origine degli animali e delle piante coinvolse raffiche di trasposizioni degli Elementi Genetici Mobili [MGE] che accelerò l’evoluzione ma, purtroppo, i dettagli di queste fasi fondamentali dell’evoluzione eucariotica sono difficili da ricostruire. Tuttavia, almeno un esempio calzante è sorprendente: l’origine delle proteine Hedgehog138, regolatori chiave dello sviluppo degli animali, da inteins139 chiamati anche “proteine introni”.
L’evoluzione dei sistemi di difesa: un segno distintivo delle transizioni evolutive
L’ubiquità e l’abbondanza di parassiti genetici assieme alla presenza di sistemi di difesa in (quasi) tutte le forme di vita cellulari suggeriscono, fortemente, che la loro co-evoluzione è stato uno degli aspetti fondamentali dell’evoluzione della vita, almeno dall’emersione delle proto-cellule ma, forse, anche dal momento della fase pre-cellulare, cioè attraverso tutte le principali transizioni. La caratteristica sorprendente ed essenziale dei sistemi di difesa, in particolare nei procarioti, è che essi stessi possiedono proprietà di elementi egoistici e/o derivano da tali elementi140. Il carattere egoistico dei sistemi di difesa si manifesta nella dipendenza dei più semplici di questi, vale a dire il sistema procariote Tossina- Antitossina (TA), l’infezione abortiva (AI) e il sistema di restrizione-modificazione (R-M)141 delle cellule in cui risiedono142. I meccanismi molecolari del sistema TA (tipo II), AI e R-M differiscono nei dettagli, ma il principio centrale è uno e lo stesso. Ciascuno di questi sistemi consiste di due (o meno frequentemente, di tre) proteine codificate da geni co-regolati ravvicinati. Il meccanismo del sistema TA e dei sistemi AI correlati è semplice ed elegante143. Una delle due proteine è una tossina che uccide la cellula a meno che la tossina sia complessata con la seconda proteina, l’antitossina. L’antitossina è molto meno stabile rispetto alla tossina e, pertanto, quando i geni TA / AI sono persi o inattivati, la tossina viene rilasciata e muore la cellula. Ciò spiega la dipendenza dei sistemi TA / AI che spesso risiedono su plasmidi, ai quali il sistema TA dota di dipendenza e sfrutta come veicoli per una diffusione orizzontale. Così, i sistemi di TA / AI in realtà rappresentano una classe speciale di MGE (o forse più precisamente, “quasi-MGE”). Anche se non codificano alcuna informazione per orientare la propria replica, promuovono la propria mobilità utilizzando l’autostop su plasmidi e facendo si che le cellule ospiti mantengano questi plasmidi.
La funzione di difesa del TA e dell’AI è realizzata tramite l’altruistica morte cellulare programmata [PCD] e la semplicità di questi sistemi è compatibile con la loro comparsa concomitante con l’origine delle proto-cellule che, sotto il concetto sviluppato qui, erano già inclini ad aggregazione (pluricellularità primitiva). Le tossine possiedono una serie di attività diverse ma la più comune è quella dell’interfase144, una RNAsi145 che scinde mRNA all’interno del ribosoma146. Gli interferases sono piccole proteine con una semplice piega che probabilmente sono state tra i primi enzimi ad evolversi. Un’altra comune tossina, ancora insufficientemente caratterizzata, componente dei sistemi di TA e AI, è una nucleotidyltransferase147, un altro, probabilmente, enzima primitivo di dimensioni minime148.
I sistemi R-M [restriction modification systems] differiscono dai sistemi Tossina-Antitossina [TA] per quanto riguarda il principio della loro azione protettiva: attaccano direttamente virus invadenti e altro DNA estraneo piuttosto che uccidere la cellula infettata149. Tradizionalmente, i sistemi R-M non sono considerati come i sistemi tossine-antitossine ma in effetti funzionano su un principio simile. In questo caso, la tossina è un DNA endonucleasi150 e l’antitossina è un methylase151 che rende il DNA ospite resistente all’endonucleasi. Il methylase e l’endonucleasi condividono rigide sequenze di specificità, in modo che quando il methylase è inattivato, l’endonucleasi diventa tossico e uccide la cellula. Inoltre, almeno alcuni moduli R-M creano dipendenza. Anche se meno accuratamente compreso che il caso del sistema TA, è stato dimostrato che quando un modulo R-M è perso da una cellula, l’attività di methylase scende più velocemente dell’attività di endonucleasi provocando una cosiddetta uccisione delle cellule post-segregazionale152.153 I moduli R-M sono spesso trasferiti su plasmidi, trasposoni e virus, e appartengono, effettivamente, alla stessa classe di “quasi-MGE” come i sistemi di TA e AI.
Sebbene i sistemi più semplici di difesa, TA, AI e RM, che rappresentano collettivamente l’immunità innata nei procarioti, possiedono proprietà dei MGE, i più complessi sistemi di immunità adattativa, in particolare CRISPR-Cas154, non sembrano mostrare direttamente tali caratteristiche155. Anche se il trasferimento orizzontale dei sistemi CRISPR-Cas è comune, non sembra causare dipendenza. Tuttavia, l’origine dell’immunità adattativa che, a sua volta, può essere considerata un passaggio evolutivo [transizione evolutiva] minore, comportò contributi sostanziali dai MGE. In particolare, il sistema CRISPR-Cas si pensa si sia evoluto attraverso la ricombinazione di un trasposone (ricordiamo che sono elementi genetici presenti nei genomi di procarioti ed eucarioti) auto-sintesi della famiglia casposon (così chiamato perché l’integrasi/trasposasi di questi elementi è un omologo della proteina CAS1, l’enzima chiave nella fase di adattamento della risposta CRISPR-Cas)156 con un ipotetica immunità locale ancestrale innata157. In effetti, le reazioni catalizzate da un’integrasi durante l’integrazione trasposoni e da CAS1 durante l’adattamento CRISPR-Cas sono meccanicamente quasi identiche158. I trasposoni sembrano essere perfetti strumenti “pre-fabbricati” per il reclutamento evolvendo i sistemi di immunità adattiva e, potenzialmente, altri meccanismi di manipolazione del genoma. Questa caratteristica dei trasposoni è sorprendentemente dimostrata dall’evoluzione parallela del CRISPR-Cas, dell’immunità adattiva dei vertebrati e dal sistema di eliminazione del DNA in ciliati159. In tutti e tre i casi, trasposoni non collegati sembrano aver donato non solo l’enzima catalizzatore del ri-arrangiamento del genoma, ma anche le ripetizioni che servono come siti di riconoscimento per questo enzima. Sorprendentemente, un gruppo diverso di trasposoni diede ulteriori contributi all’evoluzione della immunità adattativa procariote, sostituendo i moduli ancestrali delle molecole effettrici160 dei sistemi CRISPR-Cas di classe 1 con nucleasi trasposoni-derivati161. Di conseguenza, i sistemi di classe 2 del CRISPR-Cas sono completamente derivati da MGE [Elementi Genetici Mobili].
La maggior parte, se non tutti, i sistemi di difesa nei procarioti sono “pistole a noleggio” che possono funzionare sia come armi di difesa per le cellule contro i parassiti o come armi di contro-difesa (vale a dire, in realtà, di attacco) utilizzate dai parassiti contro gli organismi ospiti162. Questa dualità si estende dai moduli di difesa più semplici quali TA e R-M ai complessi sistemi immunitari quali i CRISPR-Cas. I sistemi di difesa e di contro-difesa, almeno in alcuni casi, si scontrano direttamente. Come ad esempio, è stato dimostrato che un sistema CRISPR-Cas fago-codificato abroga l’attività dei sistemi ospiti R-M, consentendo, in tal modo, la fago riproduzione163.
I sistemi di difesa semi-egoisti basati sul principio della dipendenza non sono sopravvissuti alla transizione procarioti a eucarioti, presumibilmente a causa del degrado irreversibile degli operoni in eucarioti che resero i componenti della tossina di tali sistemi altamente deleteri164. Sorprendentemente, però, componenti di questi sistemi sono stati ampiamente reclutati come le proteine eucariotiche di segnalazione e gli enzimi cromatina165 di rimodellamento-modifica166.
L’aspetto fondamentale dell’evoluzione di difesa anti-parassita è abbastanza semplice: combinazione di sostanze attive dei sistemi di difesa sono armi capaci (se non controllate) di distruggere dei genomi. Queste armi possono essere rivolte contro un parassita o contro il suo ospite e hanno il potenziale per evolversi in elementi egoistici. Nella loro forma più semplice, tali armi, in poche parole, nucleasi, molto probabilmente, si sono evolute già nel primordiale pool genetico pre-cellulare. La loro integrazione in sistemi di contro(difesa) più complessi apparentemente monitorava transizioni evolutive e per se stessa rappresentava una serie di transizioni minori. Prese insieme, tutte queste osservazioni dimostrano che l’evoluzione dei sistemi di difesa è intrinsecamente intrecciata con l’evoluzione degli elementi genetici egoisti. Il legame tra i due processi non è limitato agli effetti evidenti della corsa agli armamenti, ma coinvolge anche lo scambio perpetuo di componenti. Come discusso sopra, i MGE sembrano aver giocato un ruolo chiave in diverse grandi transizioni evolutive e questo coinvolgimento è in gran parte realizzato attraverso l’evoluzione dei sistemi di difesa.
Livelli di cooperazione tra entità biologiche
La biosfera è stata, letteralmente, dominata da virus e da altri elementi genetici mobili [MGE] e la comparsa di parassiti è stata una proprietà intrinseca dei sistemi replicatori. Questi due eventi affermano i multipli ed essenziali ruoli dei MGE nell’evoluzione della vita. Specifici contributi degli elementi egoisti alle maggiori transizioni evolutive sono stati identificati. Tali contributi sono disponibili in due forme: la corsa agli armamenti, che fa scattare importanti innovazioni nelle forme di vita cellulare (ospiti degli elementi egoistici), e il reclutamento diretto di parti di elementi egoistici per funzioni cellulari chiave. Al centro di ogni passaggio evolutivo [transizione evolutiva] c’è l’emergere di un nuovo livello della cooperazione tra entità biologiche e, quindi, di un nuovo livello di selezione. Una delle forze motrici chiave nell’evoluzione della cooperazione e della compartimentazione, che precede e facilita l’emergere di collettivi, è la difesa contro i parassiti. Un ensemble (un agglomerato di singole unità cellulari) può fare uso di meccanismi che sarebbero inaccessibili alle singole entità. Questi sono i meccanismi che comportano una componente altruistica e che permettono al collettivo di evitare il collasso sotto la pressione dei parassiti, stabilizzando il sistema ospite-parassita nel suo complesso. Un aspetto complementare della co-evoluzione ospite-parassita è la serie di “pistole a noleggio” per cui gli stessi sistemi molecolari sono utilizzati dagli ospiti e dai parassiti per la difesa e la contro-difesa rispettivamente. Queste molecole sono strumenti della manipolazione del genoma e in tale veste vanno direttamente oltre la semplice difesa, come dimostrato da molti casi di exaptation come la telomerasi eucariotica, PRP8 e varie proteine TA-derivate coinvolte nella segnalazione e nel rimodellamento della cromatina. Inoltre, la difesa è non limitata al reclutamento di “armi genomiche” e può essere asimmetrica come sottinteso dai modelli dell’origine del nucleo.
In quest’argomentazione sono state tralasciate 3 delle 7 transizioni di Szathmáry167 (tabella 1), vale a dire l’origine degli eucarioti fotosintetici che è stato precipitato dalla simbiosi tra l’antenato dell’Archaeplastida, l’origine dell’eusocialità, avvenuta indipendentemente in due gruppi di animali, insetti e mammiferi, e l’origine della società umana dotata di linguaggio. Prima di chiudere, qualche parola su queste transizioni sono dovute. I genomi di molti cianobatteri contengono introni Gruppo II, che si sono moltiplicati nei genomi dei cloroplasti168. Così, dopo l’endosimbiosi cianobatterica, il genoma ospite è stato oggetto di un attacco da questi elementi, analogo al caso dei mitocondri. In particolare, i geni derivati da cloroplasti hanno appena leggermente minore densità di introni dei geni della pianta ancestrale, cioè sono quasi saturi di introni169. Questo accumulo di introni certamente svolse un ruolo importante nell’assimilazione dei geni derivati dai cloroplasti delle cellule vegetali. Tuttavia, non è chiaro se cianobatteri Gruppo II introni hanno dato origine a questi introni, e, più in generale, non sono state rilevate impronte finora di un attacco di introni cianobatteri nei genomi delle piante o alghe. Pertanto, il ruolo degli elementi genetici mobili [MGE] nella transizione foto-sintetica rimane incerto.
L’origine dell’eusocialità e soprattutto l’origine delle società dotate di linguaggio, mentre formalmente corrispondono alla definizione di una transizione, appaiono fondamentalmente diverse da altre transizioni in quanto riguardano principalmente cambiamenti nel comportamento di macro-organismi anziché innovazioni molecolari coinvolte nelle transizioni precedenti (anche se limitati, cambiamenti molecolari, altamente specifici, certamente sono stati coinvolti nelle ultime due transizioni). Tuttavia, un ruolo delle infezioni da virus o della mobilitazione dei trasposoni nell’evoluzione degli animali sociali è immaginabile ed è, sicuramente, oggetto di ricerca interessante. Ad esempio, è immaginabile che le infezioni potrebbero essere una forza trainante per l’evoluzione dell’eusocialità negli insetti, dove la riproduzione è limitata a individui specializzati, come le regine, che potrebbero essere, specificamente, protetti. Oltre a tale presunto coinvolgimento di parassiti genetici, la suscettibilità ad altre varietà di parassiti, ad esempio, gli ectoparassiti animali, è probabile che sia un fattore importante nell’evoluzione dell’eusocialità170.
Il contributo degli elementi genetici mobili [MGE] all’evoluzione degli organismi cellulari non è per nulla limitato alle grandi transizioni. Entrambi, la diversificazione dei meccanismi di difesa e contro-difesa e l’exaptation dei MGE per le funzioni cellulari, si verificano di continuo durante tutto il corso dell’evoluzione171. Un esempio è l’origine della immunità adattativa dei vertebrati in cui un trasposone, della famiglia Transib svolse un ruolo centrale172. Altro esempio è la ripetuta exaptation dei geni delle “proteine buste”173 di retrovirus che diedero luogo a syncytins174, i recettori della placenta dei mammiferi175.
Chiaramente, la difesa dai parassiti non è l’unico fattore dietro le transizioni evolutive. Vi è almeno un ‘altra potente forza spingente l’evoluzione della cooperazione, vale a dire la produzione differenziale di “beni pubblici” (produzione e condivisione di risorse) da parte di unità che beneficiano di un insieme176. Il paradigma dei “beni pubblici” si applica a tutte le fasi nell’evoluzione della vita, tra cui ciascuna delle grandi transizioni. La produzione di tali beni potrebbe aver spinto l’origine delle prime cooperative di elementi genetici primordiali177 ed è anche rilevante per la transizione endosimbiontica in cui endosimbionti e organismi ospiti forniscono set complementari di metaboliti e proteine178. È importante sottolineare che la difesa anti-parassita e la condivisione di ‘beni pubblici’ spesso sono direttamente collegate. La distruzione di parassiti e il suicidio altruistico, da un lato, proteggono la popolazione ospitante, e dall’altro, comportano la produzione di materiali di consumo quali nucleotidi e aminoacidi. Pertanto, la differenziazione tra i fattori che guidano la cooperazione tra gli individui e un passaggio evolutivo non sempre è significativa: forse, il più delle volte, entrambi i driver sono in azione. Insieme, questi due fattori complementari e interagenti, la co-evoluzione ospite-parassita e la produzione e la condivisione di risorse (beni pubblici), potrebbe essere responsabile di molti, se non della maggior parte, degli aspetti delle transizioni evolutive.
Finalità del testo
Questa interpretazione dell’evoluzione (come processo di complessità crescente del sistema ospite-parassita), seguendo il paradigma delle transizioni evolutive di Eörs Szathmáry & John Maynard Smith nella sua ultima versione sviluppata da Eugene V. Koonin179, ha lo scopo di farci percorrere, idealmente, il crescente processo della complessità biotica, e fornire ai nostri cervelli un repertorio di modelli metaforici che ci sollecitino a rivedere, in modo critico, i modelli semplicistici somministratici dalle bio-politiche egoistiche che gestiscono i complessi sistemi “ospite-parassita”, modelli che, metaforicamente, includono le relazioni umane nelle nostre odierne popolazioni.
- Le transizioni evolutive comportano cambiamenti nel modo in cui l’informazione genetica è immagazzinata e trasmessa.
- Eörs Szathmáry & John Maynard Smith. Le origini della vita. Dalle molecole organiche alla nascita del linguaggio. Einaudi, 2001.
- In biologia (parassitologia, zoologia, botanica), l’ospite è la specie, al cui interno o sulla cui superficie vive un simbionte, che può essere un commensale, un parassita o un organismo in simbiosi mutualistica con l’ospite. L’aggettivo viene attribuito anche alla cellula (cellula ospite) nella quale si riproduce un parassita intracellulare, quale per esempio un virus.
- Perché ci sono genomi più grandi? Due ipotesi:1° Ipotesi del Bulk-DNA (Bulk = mole) (Commoner 1964; Bennett 1972; Cavalier-Smith 1978) Ipotesi del Selfish-DNA (DNA egoista) (Doolittle and Sapienza 1980; Orgel and Crick 1980) Organismi di maggiori dimensioni hanno cellule più grandi, e organismi con cellule più grandi hanno in genere genomi più grandi Avere una mole maggiore (bulk) può avere un significato adattativo perché le dimensioni del genoma definiscono quelle del nucleo, la grandezza delle cellule, il tasso di divisione, quindi nel complesso influenzano il tasso di sviluppo e la dimensione cellulare allo stadio maturo. 2° ipotesi Ipotesi del Selfish-DNA (DNA egoista) (Doolittle and Sapienza 1980; Orgel and Crick 1980) l’espansione delle dimensioni del genoma è dovuta alla proliferazione di elementi genetici egoisti -“selfish”- che si espandono finché non hanno effetto negativo sulla fitness.
- Il termine endosimbiosi deriva dal greco: e¨νδον = dentro; συν = insieme; βιος = vita, letteralmente “vita-insieme-dentro”. Già solo nel termine sono presenti tutti gli elementi che descrivono le caratteristiche principali di questo particolare tipo di relazione che si può instaurare tra organismi. Si tratta infatti della convivenza tra due specie di cui una vive all’interno dell’altra senza arrecare danno. Lo scopo di questa particolare interazione ovviamente è, per entrambe le specie coinvolte, quello di ottenere vantaggi in termini di sopravvivenza. Le cellule eucariotiche per come le conosciamo presentano una complessità strutturale dovuta alla presenza di numerosi organelli che svolgono le più differenti funzioni per il mantenimento della vita. Le prime cellule eucariotiche, quelle primordiali, dovevano apparire relativamente semplici e prive di molte di queste strutture. In pratica somigliavano a dei procarioti. Secondo la teoria dell’endosimbiosi, le attuali cellule eucariotiche (piene zeppe di organelli come per esempio mitocondri o cloroplasti) si sono formate grazie all’unione di cellule più semplici, i batteri simbionti, in grado di svolgere da soli alcune funzioni peculiari, come estrarre energia dai composti organici attraverso meccanismi di respirazione aerobica. Questa funzione non era propria di quelle cellule eucariotiche “primitive”. Esse la acquisirono, probabilmente più di 1,2 miliardi di anni fa, dopo aver inglobato i suddetti batteri aerobi. Ovviamente non tutti i batteri resistettero alla digestione messa in atto dalle cellule che li avevano inglobati, ma quelli che sopravvissero godettero dei vantaggi di vivere in un ambiente protetto e ricco di nutrienti (l’interno della cellula). Queste condizioni fecero sì che col tempo gli stessi batteri divennero completamente dipendenti dalla cellula che li aveva inglobati; analogamente quest’ultima otteneva in cambio una fornitura extra di energia (attraverso i processi di produzione di ATP propri della respirazione). Un grosso vantaggio evolutivo per entrambi. Analogamente, l’introduzione di un batterio fototrofo ossigenico (capace cioè di convertire l’energia solare in energia chimica producendo ossigeno gassoso) ha conferito proprietà fotosintetiche a una primitiva cellula eucariotica. Negli anni ‘80 la biologa americana Lynn Margulis propose questa teoria, che spiega l’origine di organelli come i mitocondri e i cloroplasti all’interno della cellula eucariotica. Tale teoria è ritenuta attendibile anche grazie a importanti conferme sperimentali riguardanti i due organelli, come ad esempio: 1. la presenza del materiale genetico proprio al loro interno, in forme circolari di DNA (tipiche dei procarioti); 2. la presenza sulle membrane dei ribosomi di tipo procariotico con sequenze di RNA specifiche di alcuni batteri; 3. il DNA è in grado di auto replicarsi ed essi si dividono indipendentemente dalla cellula; 4. entrambi sono circondati da due membrane, la più interna delle quali mostra una composizione simile a quella di una membrana cellulare procariotica; 5. entrambi gli organelli subiscono inibizione delle loro funzioni se trattati con gli stessi antibiotici che inibiscono (in vivo) la funzionalità dei batteri. http://www.oilproject.org/lezione/mitocondri-cloroplasti-endosimbiosi-cellula-energia-atp-eucarioti-procarioti-4979.html.
- Il concetto di forma transizionale è una conseguenza della teoria evoluzionistica introdotta da Darwin, che ipotizzava una lenta e progressiva trasformazione degli esseri viventi. Wikipedia.
- Darwin C. On the origin of species. Murray, London, 1859.
- Dobzhansky T. Genetics and the origin of species. Columbia University Press. New York, 1937 / Huxley JS. Evolution: the modern synthesis. Allen and Unwin. London, 1942.
- L’insieme dei cambiamenti che si realizzano lungo le linee di discendenza degli esseri viventi. In biologia, con il termine evoluzione, si intende il progressivo ed ininterrotto accumularsi di modificazioni successive, fino a manifestare, in un arco di tempo sufficientemente ampio, significativi cambiamenti morfologici, strutturali e funzionali negli organismi viventi. L’evoluzione graduale si basa sulla trasmissione del patrimonio genico di un organismo individuale alla sua progenie e sull’interferenza in essa frapposta dalle mutazioni casuali. Sebbene i cambiamenti tra una generazione e l’altra siano generalmente piccoli, il loro accumularsi nel tempo può portare un cambiamento sostanziale nella popolazione, attraverso i fenomeni di selezione naturale e deriva genetica, fino all’emergenza di nuove specie.
- Szathmáry E, Maynard Smith J. From replicators to reproducers: the first major transitions leading to life. Journal of Theoretical Biology. 187, 555–571. 1997 / Maynard Smith J, Szathmáry E. The major transitions in evolution. W. H. Freeman. New York, 1995 / Maynard Smith J. The units of selection. Novartis Found Symp. 213, 203–211. 1998 / Szathmáry E. Biological information, kin selection, and evolutionary transitions. Theor. Popul. Biol. 59, 11–14. 2001 / Szathmáry E. Toward major evolutionary transitions theory 2.0. Proceedings of the National Academy of Sciences of the USA Vol. 112, no. 33: 10104–10111. 2015.
- Szathmáry E. Toward major evolutionary transitions theory 2.0. Proc. Natl Acad. Sci. USA 112, 10 104–10 111. 2015.
- Termine che indica la prima struttura vivente dotata di acidi nucleici e proteine, circondata da una membrana di lipidi, isolata selettivamente dall’esterno e capace di autoreplicarsi. Per i ricercatori interessati a ricostruire i primissimi stadi dell’evoluzione è una sfida capire come abbiano avuto origine gli organismi viventi primordiali e come questi effettuassero il processo della replicazione. La scoperta delle proprietà catalitiche dell’RNA ha dimostrato che una singola specie chimica può funzionare sia come genoma sia come catalizzatore e ha suggerito che ci sia stata una fase, prima dell’evoluzione delle attuali cellule, in cui genomi costituiti da RNA erano replicati da enzimi fatti di RNA: un mondo a RNA. Per molto tempo si è ritenuto che soltanto gli acidi nucleici fossero in grado di immagazzinare e replicare le informazioni genetiche e che soltanto le proteine potessero funzionare da catalizzatori. Ciò rendeva difficile immaginare come potevano essersi evolute le cellule odierne. Nel nostro mondo, il mondo a DNA, i genomi formati da DNA si replicano tramite enzimi costituiti da proteine e il DNA fornisce l’informazione per la sintesi delle proteine stesse. Un sistema vivente primordiale basato soltanto su DNA o su proteine era inconcepibile ed era altamente improbabile ipotizzare che il DNA e la sintesi delle proteine su stampo avessero avuto origine nello stesso momento. La dimostrazione che l’RNA poteva funzionare come catalizzatore risolse il problema ‘dell’uovo e della gallina’ che aveva assillato la biologia evolutiva. Inoltre, ciò richiamò l’attenzione dei biologi sul fatto che le attuali cellule possono essere viste come una sorta di archivio della storia evolutiva della cellula. In base a ciò, in pochi anni le nostre conoscenze sull’evoluzione cellulare hanno fatto un gigantesco passo in avanti. Adesso possiamo rappresentare le prime fasi dell’evoluzione con uno schema molto semplice: reazioni prebiotiche sulla Terra primordiale hanno generato l’RNA; l’RNA è divenuta la prima molecola in grado di autoreplicarsi; si sono sviluppati esseri viventi con genoma a RNA e sistemi biochimici relativamente semplici; questi si sono poi evoluti in organismi più complessi, in grado di sintetizzare proteine, per divenire infine le cellule moderne con genomi a DNA e apparati biochimici estremamente sofisticati che noi conosciamo. (*)http://www.treccani.it/enciclopedia/protocellula_(Enciclopedia-della-Scienza-e-della-Tecnica)/
- Ibidem
- Bass LW. The evolution of individuality. Princeton University Press, Princeton, 1988.
- Corning PA, Szathmáry E. ‘Synergistic selection’: a Darwinian frame for the evolution of complexity. J. Theor. Biol. 371, 45–58. 2015.
- Turchin VF. The phenomenon of science: a cybernetic approach to human evolution. Columbia University Press, New York, 1977.
- In genetica, si definiscono elementi trasponibili (chiamati anche elementi genetici mobili; in inglese MGE – Mobile genetic elements) dei segmenti di DNA capaci di spostarsi e inserirsi in diverse posizioni del genoma, tramite un meccanismo chiamato trasposizione. Scoperti la prima volta negli anni cinquanta, sono oggetto di interesse scientifico per la loro capacità di provocare mutazioni genetiche, a causa dei loro spostamenti casuali nel genoma. Sono presenti nei genomi sia procariotici che eucariotici. Wikipedia.
- Koonin EV, Dolja VV. A virocentric perspective on the evolution of life. Current Opinion in Virology. 3 (5) 546-557. 2013.
- May RM, Anderson RM. Parasite–host coevolution. Parasitology 100(Suppl. 1), S89-101. 1990 Messinger SM, Ostling A. The consequences of spatial structure for the evolution of pathogen transmission rate and virulence. American Naturalist. Vol. 174, Issue 4, 441– 454. 2009 / Koskella B, Brockhurst MA. Bacteria–phage coevolution as a driver of ecological and evolutionary processes in microbial communities. FEMS Microbiology Review. 38 (5): 916-931. 2014 / Leggett HC, Brown SP, Reece SE. War and peace: social interactions in infections. Philosophical Transactions of the Royal Society B 369, 20130365. 2014 / Gorter FA, Hall AR, Buckling A, Scanlan PD. Parasite host range and the evolution of host resistance. Journal of Evolutionary Biology. 28 (5): 1119-1130. 2015.
- La corsa agli armamenti evolutiva (evolutionary arms race, tradotta anche come corsa evolutiva agli armamenti) consiste in un miglioramento della propria linea genealogica per poter sopravvivere, come diretta conseguenza dei miglioramenti di altre linee genealogiche. È un tipo di co-evoluzione. In termini più semplice si tratta di un tipo di competizione, fra due o più organismi, della stessa o di diverse specie, i quali presentano, nel corso del tempo, degli adattamenti che gli permetteranno, sempre con maggiore efficienza, di riuscire a resistere, se non in alcuni casi a vincere, la sfida. Fatte queste premesse, si può dire che si tratta di un potente motore dell’evoluzione. Questo concetto è stato definito da Richard Dawkins. Il nome scelto per questo fenomeno è ispirato all’omonimo fenomeno, tutto umano, dell’affrettarsi a produrre e sviluppare il maggior numero di armi e tecnologie militari, nel minore tempo possibile.
- Forterre P, Prangishvili D. The great billion-year war between ribosome- and capsidencoding organisms (cells and viruses) as the major source of evolutionary novelties. Annals of the New York Academy of Science, 1178, 65–77. 2009 / Forterre P, Prangishvili D. The major role of viruses in cellular evolution: facts and hypotheses. Current Opinion in Virology. 3 (5): 558-565. 2013 / Edgell DR, Chalamcharla VR, Belfort M. Learning to live together: mutualism between selfsplicing introns and their hosts. BMC Biology. 9, 22. 2011 / Koonin EV, Krupovic M. A movable defense. The Scientist. 2015.
- L’adattamento degli organismi è stato identificato con due diversi criteri: il fattore storico riconosciuto ad opera della selezione naturale nel corso dei processi evolutivi e quello che adesso aumenta le caratteristiche di sopravvivenza indipendentemente da come siano comparse nella storia. Per definire questi caratteri, non modellati dalla selezione naturale che oggi aumentano la capacità di sopravvivenza è stato utilizzato il termine exaptations (exattamento) per preservare il termine adattamento ai processi di selezione naturale darwiniani.
- Bao X, Roossinck MJ. A life history view of mutualistic viral symbioses: quantity or quality for cooperation? Current Opinion in Microbiology. 16 (4): 514-518. 2013 / Shirogane Y, Watanabe S, Yanagi Y. Cooperation: another mechanism of viral evolution. Trends in Microbiology, 21 (7): 320-324. 2013.
- Kazazian Jr HH. Mobile elements: drivers of genome evolution. Science 303, 1626–1632. 2004 / Goodier JL, Kazazian Jr HH. Retrotransposons revisited: the restraint and rehabilitation of parasites. Cell 135, 23–35. 2008 / Hua-Van A, Le Rouzic A, Maisonhaute C, Capy P. Abundance, distribution and dynamics of retrotransposable elements and transposons: similarities and differences. Cytogenet. Genome Res. 110, 426–440. 2005 / Jurka J, Kapitonov VV, Kohany O, Jurka MV. Repetitive sequences in complex genomes: structure and evolution. Annual Review of Genomics and Human Genetics. Vol. 8: 241-259. 2007 / Huda A, Jordan IK. Epigenetic regulation of Mammalian genomes by transposable elements. Annals of the New York Academy of Science. 1178, 276-284. 2009 / Werren JH. Selfish genetic elements, genetic conflict, and evolutionary innovation. Proceeding of the National Academy of Sciences of the USA. 108 (Suppl. 2), 10863-70. 2011 / Lopez-Flores I, Garrido-Ramos MA. The repetitive DNA content of eukaryotic genomes. Genome Dynamics. 7, 1-28. 2012.
- Miller WJ, Capy P. Mobile genetic elements as natural tools for genome evolution. Methods in Molecular Biology, 260, 1-20. 2004 Levin HL, Moran JV. Dynamic interactions between transposable elements and their hosts. Nature Reviews. Genetics. 12 (9): 615-627. 2011.
- La trasduzione batterica consiste nel passaggio del DNA di un batterio ad un altro tramite un fago. Questo processo permette il passaggio di materiale genetico da una cellula ad un’altra; è quindi uno dei meccanismi di ricombinazione genetica dei batteri (insieme alla coniugazione batterica e alla trasformazione batterica), ma anche del fenomeno del trasferimento orizzontale dei geni.
- Con il termine fotosistema si fa riferimento ad un complesso molecolare incluso nella membrana dei tilacoidi e attivo nella fase luminosa della fotosintesi. Questi fotosistemi sono infatti ammassi di molecole (200-300) contenenti pigmenti fotosintetici, cioè clorofille e carotenoidi (pigmenti verdi), che hanno il compito di assorbire l’energia luminosa: quando infatti un pigmento viene colpito da un fotone e ne assorbe l’energia, uno dei suoi elettroni viene eccitato e salta su un livello elettronico a energia maggiore. Quasi immediatamente l’elettrone torna al livello di energia originario e, durante questo processo, l’energia in più che aveva acquistato viene liberata, e passa da una molecola di pigmento all’altra, finché arriva a una coppia di particolari molecole di clorofilla che funzionano da trappola per l’energia. L’energia così intrappolata provoca il trasferimento di un elettrone da una di queste molecole a una molecola che funge da accettatore. Da un punto di vista biochimico, i fotosistemi sono delle ossidoreduttasi luce-dipendenti. Nei batteri fotosintetici, si trova un solo tipo di fotosistema, mentre nei cianobatteri e in tutti i vegetali eucarioti fotosintetici se ne trovano due tipi che lavorano in serie e sono denominati I (primo) e II (secondo).
- Sullivan MB, Lindell D, Lee JA, Thompson LR, Bielawski JP, Chisholm SW. Prevalence and evolution of core photosystem II genes in marine cyanobacterial viruses and their hosts. PLoS Biology 4 (8), e234. 2006 / Lindell D et al. Genome-wide expression dynamics of a marine virus and host reveal features of co-evolution. Nature 449, 83–86. 2007.
- Lang AS, Zhaxybayeva O, Beatty JT. Gene transfer agents: phage-like elements of genetic exchange. Nature Review. Microbiology. 10 (7): 472-482. 2012.
- Cortez D, Forterre P, Gribaldo S. A ridde reservoir of integrative elements is the major source of recently acquired foreign genes and ORFans in archaeal and bacterial genomes. Genome Biology. 10, R65. 2009.
- Jalasvuori M. Vehicles, replicators, and intercellular movement of genetic information: evolutionary dissection of a bacterial cell. International Journal of Evolutionary Biology. Vol.2012, Article ID 874153. 2012 / Jalasvuori M, Koonin EV. Classification of prokaryotic genetic replicators: between selfishness and altruism. Annals of the New York Academy of Sciences. 1341, 96-105. 2015 / Koonin EV, Starokadomskyy P. Are viruses alive? The replicator paradigm sheds a decisive light on an old but misguided question. Studies in History and Philosophy of Biological and Biomedical Sciences. Vol. 56, pp. 125-134. 2016.
- Si definiscono trasposoni alcuni elementi genetici presenti nei genomi di procarioti ed eucarioti, capaci di spostarsi da una posizione all’altra del genoma. In particolare nei procarioti essi possono spostarsi in posizioni nuove nel medesimo cromosoma (perché unico) oppure su plasmidi o fagi, mentre negli eucarioti essi possono spostarsi sia in posizioni diverse sullo stesso cromosoma sia su cromosomi differenti. Essi fanno parte degli elementi trasponibili, assieme alle sequenze di inserzione IS. Questo processo di trasferimento è noto come trasposizione e richiede la presenza di siti per la ricombinazione del DNA, posti sia sul trasposone che sul cromosoma bersaglio, e l’azione di specifici enzimi, detti trasposasi. In seguito alla trasposizione si può avere l’inattivazione funzionale di un gene, nel caso in cui il trasposone si inserisca in questo gene, o la modificazione dei livelli di espressione di un gene, nel caso in cui il trasposone si inserisca nel promotore del gene.
- Koonin EV, Dolja VV. Virus world as an evolutionary network of viruses and capsidless selfish elements. Microbiology and Molecular Biology Review. 78 (2): 278-303. 2014.
- Un provirus è un genoma virale che si è integrato nel DNA della cellula ospitante, in modo tale che quest’ultima non viene distrutta ma, allorché si duplica, può trasmettere il genoma virale alle cellule discendenti. Fra gli esempi di provirus si citano i retrovirus e i profagi.
- Canchaya C, Fournous G, Chibani-Chennoufi S, Dillmann M-L, Bru¨ssow H. Phage as agents of lateral gene transfer. Current Opinion in Microbiology. 6 (4): 417-424. 2003 / Łos´ M, Wegrzyn G. Pseudolysogeny. Advances in Virus Research. 82, 339-349. 2012 / Sherwood R, Casjens SR, Hendrix RW. Bacteriophage lambda: early pioneer and still relevant. Virology, 479-480, 310–330. 2015.
- Mayer J, Meese E. Human endogenous retroviruses in the primate lineage and their influence on host genomes. Cytogenetic and Genome Research. 110 (1-4): 448-456. 2005 / Friedli M, Trono D. The developmental control of transposable elements and the evolution of higher species. Annual Review of Cell and Developmental Biology. 31, 429-451. 2015.
- Briani F, Deho` G, Forti F, Ghisotti D. 2001 The plasmid status of satellite bacteriophage P4. Plasmid 45 (1): 1-17.
- Suttle CA. Viruses in the sea. Nature 437, 356–361. 2005 / Suttle CA. Marine viruses–major players in the global ecosystem. Nature Review Microbiology 5, 801-812. 2007 / Rohwer F, Thurber RV. Viruses manipulate the marine environment. Nature 459, 207–212. 2009 / Ignacio-Espinoza JC, Solonenko SA, Sullivan MB. 2013 The global virome: not as big as we thought? Current Opinion in Virology 3, 566-571.
- Forterre P. Manipulation of cellular syntheses and the nature of viruses: the virocell concept. Comptes Rendus Chimie, Volume 14, Issue 4, Pages 392-399, 2010 / Forterre P. The virocell concept and environmental microbiology The ISME Journal (Multidisciplinary Journal of Microbial Ecology), 7(2): 233-236, 2013.
- I virus sono stati storicamente definite come particelle virali (virioni). Il concetto di virocell è stato proposto per mettere invece l’accento sul ciclo intracellulare della riproduzione dei virus. In questo punto di vista, l’infezione virale trasforma le cellule infette (o un batterio, un archaeon o eucariote) in un nuovo tipo di organismo cellulare, un virocell, il cui scopo è quello di produrre virioni. Il concetto virocell ha diverse implicazioni per la questione dell’origine e della natura del virus. Questo approccio sottolinea che i virus hanno origine nei ribosomi codificanti (ribocells) e possono essere considerati autentici organismi cellulari viventi. In particolare, il concetto virocell aiuta a capire che nuove proteine potrebbero provenire da due diversi contesti cellulari (sia ribocell che virocell) durante la replica / ricombinazione del genoma. Considerando la diversità, l’ubiquità e l’abbondanza di virus, una grande percentuale delle proteine nella biosfera hanno, quindi, probabilmente e autenticamente, origine virale. Molti di loro furono in seguito trasferite ai genomi di ribocells attraverso integrazioni virali o di plasmidi. Il concetto di virocell contribuisce così a farci comprendere il ruolo fondamentale che i virus hanno giocato nell’evoluzione biologica. I virocells corrispondono a cellule infette che producono virioni. Il virus è un essere vivente durante la fase intracellulare del suo ciclo di vita. Virocell Concept, The. Forterre Patrick, Univ Paris-Sud, CNRS UMR, Orsay Cedex, Francia, pubblicato online: luglio 2012.
- Szathmáry E. Toward major evolutionary transitions theory 2.0. Proc. Natl Acad. Sci. USA 112, 10 104–10 111. 2015.
- La sintesi proteica detta anche traduzione, è il processo biochimico attraverso il quale l’informazione genetica contenuta nel mRNA (RNA messaggero), viene convertita in proteine che svolgono nella cellula un’ampia gamma di funzioni. La sintesi proteica inizia da un filamento di mRNA, prodotto a partire da un gene sul DNA attraverso il processo di trascrizione. Questo filamento è usato come stampo per la produzione di una specifica proteina. In biologia molecolare, la trascrizione è il processo mediante il quale le informazioni contenute nel DNA vengono trascritte enzimaticamente in una molecola complementare di RNA. Concettualmente, si tratta del trasferimento dell’informazione genetica dal DNA all’RNA. Nel caso in cui il DNA codifichi una proteina, la trascrizione è l’inizio del processo che porta, attraverso la produzione intermedia di un mRNA, alla sintesi di peptidi o proteine funzionali.
- Replicator: l’unità di base teorica dell’evoluzione nella visone geni-centrica dell’evoluzione.
- Szathmáry E, Demeter L. Group selection of early replicators and the origin of life. Journal of Theoretical Biology. 128 (4): 463-486, 1987 / Szathmáry E. Viral sex, levels of selection, and the origin of life. Journal of Theoretical Biology. 159 (1): 99-109, 1992 / Koonin EV, Martin W. On the origin of genomes and cells within inorganic compartments. Trends in Genetics. 21 (12): 647-654, 2005 / Takeuchi N, Hogeweg P. Evolutionary dynamics of RNA-like replicator systems: a bioinformatic approach to the origin of life. Physics of Life Reviews. 9 (3): 219-263, 2012.
- Enzima capace di duplicare una catena di DNA o RNA. Replicasi è, anche, il termine generale per una qualunque polimerasi che duplica i cromosomi, detta anche replicasi cromosomica.
- I virus imbroglioni sono stati scoperti nel corso di esperimenti in vitro che hanno dimostrato come l’inganno influenza il loro successo riproduttivo e di conseguenza la fitness riproduttiva di questi microrganismi
- Ricordiamo che i virus sono entità biologiche elementari con caratteristiche di parassiti obbligati, in quanto si replicano, esclusivamente, all’interno delle cellule viventi di altri organismi.
- Haruna I, Spiegelman S. Autocatalytic synthesis of a viral RNA in vitro. Science 150: 884-886. 1965 / Spiegelman S, Haruna I, Pace NR, Mills DR, Bishop DHL, Claybrook JR, Peterson R. Studies in the replication of viral RNA. Journal of Cellular Physiology. 70 (Suppl. 1): 35-64. 1967 / Spiegelman S. An approach to the experimental analysis of precellular evolution. Quarterly Reviews of Biophysics. Vol. 4, Issue 2-3: 213-253. 1971.
- Mills DR, Kramer FR, Spiegelman S. Complete nucleotide sequence of a replicating RNA molecule. Science 180, 916–927. 1973
- Koonin EV, Martin W. On the origin of genomes and cells within inorganic compartments. Trends in Genetics. 21 (12): 647-654, 2005 / Koonin EV, Senkevich TG, Dolja VV. The ancient Virus World and evolution of cells. Biology Direct 1, 29. 2006 / Koonin EV. On the origin of cells and viruses: primordial virus world scenario. Annals of the New York Academy of Sciences. 1178, 47-64. 2009 / Koonin EV. The origins of cellular life. Antonie Van Leeuwenhoek 106 (1): 27-41. 2014
- Koonin EV, Dolja VV. A virocentric perspective on the evolution of life. Current Opinion in Virology. 3 (5) 546-557. 2013.
- Takeuchi N, Hogeweg P. The role of complex formation and deleterious mutations for the stability of RNA-like replicator systems. Journal of Molecular Evolution. Vol. 65, Issue 6: pp. 668-686. 2007 / Higgs PG, Lehman N. The RNA world: molecular cooperation at the origins of life. Nature Reviews Genetics. 16, 7-17. 2015.
- Takeuchi N. & Hogeweg P. op. cit. 2007 / Takeuchi N, Hogeweg P, Koonin EV. On the origin of DNA genomes: evolution of the division of labor between template and catalyst in model replicator systems. PLoS Computational Biology. 7, 2011 / Takeuchi N, Hogeweg P. Evolutionary dynamics of RNA-like replicator systems: a bioinformatic approach to the origin of life. Physics of Life Reviews. 9 (3): 219-263, 2012.
- Shay JA, Huynh C, Higgs PG. The origin and spread of a cooperative replicase in a prebiotic chemical system. Journal of Theoretical Biology. 364, 249–259. 2015 & Higgs PG, & Lehman N. 2015.
- Szathmáry E, & Maynard Smith J. op. cit. 1997 & Szathmáry E, & Demeter L. op. cit. 1987.
- Koonin EV, Dolja VV. A virocentric perspective on the evolution of life. Current Opinion in Virology. 3 (5): 546-557, 3013 / Forterre P. The virocell concept and environmental microbiology The ISME Journal (Multidisciplinary Journal of Microbial Ecology), 7(2): 233-236, 2013.
- Forterre P. Manipulation of cellular syntheses and the nature of viruses: the virocell concept. Comptes Rendus Chimie, Volume 14, Issue 4, Pages 392-399, 2010 / Forterre P. The virocell concept and environmental microbiology The ISME Journal (Multidisciplinary Journal of Microbial Ecology), 7(2): 233-236, 2013 / Forterre P. The origin of viruses and their possible roles in major evolutionary transitions. Virus Research. 117 (1), 5-16. 2006 / Forterre P. Three RNA cells for ribosomal lineages and three DNA viruses to replicate their genomes: a hypothesis for the origin of cellular domain. Proceeding of the National Academy of Sciences of the USA 103, 3669–3674. 2006.
- In biologia molecolare, la trascrizione è il processo mediante il quale le informazioni contenute nel DNA vengono trascritte enzimaticamente in una molecola complementare di RNA. Concettualmente, si tratta del trasferimento dell’informazione genetica dal DNA all’RNA.
- La retrotrascrizione (o trascrizione inversa) è la capacità da parte di particolari enzimi di sintetizzare una molecola di DNA a partire da RNA. L’enzima responsabile di questa caratteristica viene chiamato trascrittasi inversa, e deve il nome proprio al fatto che è in grado di compiere il passaggio inverso rispetto agli altri enzimi responsabili della trascrizione, che cioè sintetizzano RNA a partire da DNA, costituendo così una eccezione al dogma centrale della biologia molecolare.
- Gli eucarioti (Eukaryota) sono uno dei due domini tassonomici della classificazione scientifica degli esseri viventi. Costituiscono il dominio più complesso e includono cinque regni: animali, funghi, piante, protisti e cromisti. Il criterio per la distinzione dall’altro dominio, i procarioti, è la presenza di un nucleo cellulare ben definito e isolato dal resto della cellula tramite una membrana, contenente la maggior parte del materiale genetico rappresentato dal DNA (una parte minore è contenuta nei mitocondri).
- La sintesi proteica (detta anche traduzione) è il processo biochimico attraverso il quale l’informazione genetica contenuta nel mRNA (RNA messaggero), viene convertita in proteine che svolgono nella cellula un’ampia gamma di funzioni. La sintesi proteica inizia da un filamento di mRNA, prodotto a partire da un gene sul DNA attraverso il processo di trascrizione. Questo filamento è usato come stampo per la produzione di una specifica proteina.
- Il termine “bet hedging” descrive il modo in cui gli organismi riescono ad assicurare la sopravvivenza della loro specie in ambienti in rapida evoluzione, generando una progenie capace di sopravvivere in condizioni di vita diverse.
- Stewart FM, Levin BR. The population biology of bacterial viruses: why be temperate. Theoretical Population Biology. 26 (1): 93-117. 1984 Maslov S, Sneppen K. Well-temperate phage: optimal bet-hedging against local environmental collapses. Scientific Reports. 5, 10523. 2015.
- Forterre P. Three RNA cells for ribosomal lineages and three DNA viruses to replicate their genomes: a hypothesis for the origin of cellular domain. Proceeding of the National Academy of Sciences of the USA 103, 3669–3674. 2006.
Villarreal LP, DeFilippis VR. A hypothesis for DNA viruses as the origin of eukaryotic replication proteins. Journal of Virology. 74, 7079–7084. 2000 - Il pool genico (o pool genetico) di una specie o di una popolazione è l’insieme di tutti gli alleli dell’intero set di geni che appartengono a tutti gli individui che compongono una popolazione in un determinato momento. È un termine molto utilizzato nella genetica delle popolazioni.
- Il trasferimento di geni orizzontale o trasferimento genico orizzontale, conosciuto come HGT (horizontal gene transfer), è un processo nel quale un organismo trasferisce materiale genetico ad una altra cellula non discendente. Il suo contrario è il trasferimento verticale, vale a dire il fenomeno della riproduzione, col quale un organismo riceve il materiale genetico dei suoi antenati dai suoi genitori. La maggior parte degli studi sopra la genetica si sono incentrati in prevalenza sul trasferimento verticale, ma attualmente c’è la sensazione che il trasferimento orizzontale sia un fenomeno significativo. Il trasferimento artificiale di geni orizzontali è una forma di ingegneria genetica.
- Jalasvuori M, & Koonin EV. Op. cit. 2015 & Koonin EV, Martin W. op. cit. 2005.
- Embley TM, Martin W. Eukaryotic evolution, changes and challenges. Nature 440, 623–630. 2006 / Koonin EV. The logic of chance: the nature and origin of biological evolution. FT press. Upper Saddle River, NJ, 2011 / Lane N. The vital question: energy, evolution, and the origins of complex life. W.W.Norton & Company. London, 2015.
- Gli archei o archibatteri o archeobatteri (Archaea o Archaeobacteria) sono una suddivisione sistematica fondamentale, al più basso livello, della vita cellulare. Possono considerarsi regno o dominio a seconda degli schemi classificativi, ma mostrano strutture biochimiche tali da considerarsi un ramo basilare, presto distaccatosi dalle altre forme dei viventi.
- Gli organuli, o organelli, sono strutture provviste di membrana presenti all’interno della cellula eucariota, che svolgono differenti funzioni necessarie alla sua sopravvivenza. Gli organelli, assieme al citosol, formano il citoplasma.
- Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P. Molecular biology of the cell. Garland Science. New York, 2002.
- Koonin EV. Evolution of genome architecture. The International Journal of Biochemistry & Cell Biology Volume 41, Issue 2, February 2009, Pages 298-306. 2009 / Lane N, Martin W. The energetics of genome complexity. Nature 467, 929–934. 2010.
- Koonin EV. op. cit. 2009 & Palazzo AF, & Gregory TR. The case for junk DNA. PLoS Genetics. 10 (5): e1004351. 2014.
- Elliott TA, Gregory TR. What’s in a genome? The C-value enigma and the evolution of eukaryotic genome content. Philosophical Transactions of the Royal Society B. 370, 20140331. 2015.
- Rogozin IB, Carmel L, Csuros M, Koonin EV. Origin and evolution of spliceosomal introns. Biology Direct 7, 11. 2012.
- Si definiscono introni le regioni non codificanti di un gene che, insieme agli esoni, vengono trascritte dalle RNA polimerasi.
- Gli esoni costituiscono, insieme agli introni, la porzione di un gene (eucariotico o di archeobatteri) che viene trascritta dalle RNA polimerasi durante il processo di trascrizione.
- Lo spliceosoma è un grosso complesso enzimatico formato da proteine e piccole molecole di RNA nucleare (snRNA, small nuclear RNA).
- Koonin EV, Csuros M, Rogozin IB. Whence genes in pieces: reconstruction of the exon-intron gene structures of the last eukaryotic common ancestor and other ancestral eukaryotes. Wiley Interdisciplinary Reviews RNA 4 (1): 93-105. 2013.
- Il termine proteoma è usato per descrivere l’insieme delle proteine di un organismo o di un sistema biologico, ovvero le proteine prodotte dal genoma. Il termine è stato applicato a diversi tipi di sistemi biologici. Il termine deriva dalla fusione delle due parole ‘proteina’ e ‘genoma’, che sta a indicare l’insieme di tutte le proteine espresse dal genoma di un organismo. Diversamente dal genoma, che è un’entità relativamente stabile, il proteoma è un’entità dinamica, perché costantemente variabile nel corso del tempo. Considerando, per es., il proteoma di una cellula, in diversi momenti della sua vita saranno presenti diverse proteine. All’interno di un intero organismo, inoltre, sono presenti molti tipi cellulari diversi, ognuno caratterizzato da un peculiare proteoma, a seconda del tessuto di appartenenza. Le proteine, inoltre, sono in numero superiore ai geni, a causa dei numerosi meccanismi che possono intervenire nelle fasi di trascrizione del DNA.
- Il cosiddetto alternative splicing è il meccanismo più importante, che consiste nella possibilità di leggere in modo diverso l’RNA-messaggero trascritto a partire dal DNA. Esistono poi altri meccanismi che possono agire dopo la sintesi delle proteine stesse, modificando caratteristiche strutturali e quindi funzionali (per es., fosforilazione, glicosilazione, metilazione). La conoscenza del proteoma richiede quindi di andare oltre la semplice sequenza nucleotidica del genoma e la costituzione amminoacidica delle proteine, perché le caratteristiche strutturali di questi elementi, nonché le loro numerose interazioni reciproche, ne modificano in modo importante la funzione. Per queste ragioni, la cosiddetta proteomica − lo studio del proteoma − può caratterizzare un organismo e il suo comportamento in modo più preciso rispetto al solo studio del genoma.
- In biologia molecolare e in genetica, splicing (dall’inglese: montaggio) è una modifica del nascente pre-mRNA che avviene insieme o dopo la trascrizione, nella quale gli introni sono rimossi e gli esoni vengono uniti. Ciò è necessario per il tipico RNA messaggero prima che possa essere usato per produrre una corretta proteina tramite la traduzione o sintesi proteica. La maggior parte dei geni eucariotici sono costituiti da regioni codificanti (esoni) alternate a regioni non codificanti (introni). Queste ultime devono necessariamente essere rimosse dal trascritto primario per consentire la corretta traduzione e sintetizzare la proteina corrispondente. Alcuni introni sono presenti anche nei geni degli Archea, mentre sono assenti in quelli degli eubatteri. Dopo la trascrizione da parte della RNA polimerasi il trascritto primario va incontro a numerose modificazioni.
- Martin W, Koonin EV. Introns and the origin of nucleus-cytosol compartmentation. Nature 440, 41–45. 2006 / Koonin EV. The origin of introns and their role in eukaryogenesis: a compromise solution to the introns-early versus introns-late debate? Biology Direct 1, 22. 2006 & López-García P, Moreira D. Selective forces for the origin of the eukaryotic nucleus. Bioessays 28 (5): 525-533. 2006.
- Embley TM, Martin W. Eukaryotic evolution, changes and challenges. Nature 440, 623–630. 2006.
- I Proteobacteria (o proteobatteri) sono un phylum di batteri. Includono un’ampia gamma di agenti patogeni parassiti, come Escherichia coli, Salmonella typhi, Vibrio cholerae, Helicobacter pylori e molti altri. Altri sono liberi nell’ambiente e sono azotofissatori. Il gruppo viene definito principalmente in termini di RNA ribosomico ed è così chiamato per il dio greco Proteo (che è anche il nome di un genere di batteri tra i proteobatteri) in grado di cambiare forma a causa della diversità delle forme riscontrabili.
- Lokiarchaeota è un nuovo phylum che si propone di integrare la sistematica delle Archaea. A quanto pare include microbi il cui aspetto visivo è ancora sconosciuto, ma è stato identificato dall’analisi genetica. La sua importanza deriva dall’analisi filogenetica che dimostra l’esistenza di un gruppo monofiletica composto da lokiarchaeotas insieme ed eucarioti, per cui si ritiene che questo microorganismo sia l’anello mancante tra eucarioti e l’origine procariotica. La presenza di diversi geni di funzioni associate alla membrana cellulare, fornisce spunti per l’ipotesi dell’accoglienza dell’Archeano, sostenendo l’ipotesi dell’eocyte per l’origine e l’evoluzione degli eucarioti.
- Spang A et al. Complex archaea that bridge the gap between prokaryotes and eukaryotes. Nature 521, 173–179. 2015 / Embley TM, Williams TA. Evolution: steps on the road to eukaryotes. Nature 521, 169–170. 2015 / Koonin EV. Archaeal ancestors of eukaryotes: not so elusive any more. BMC Biology 13, 84. 2015 / Godfrey-Smith P. Reproduction, symbiosis, and the eukaryotic cell. Proceeding of the National Academy of Sciences of the USA. Vol. 112, no. 33, 10 120-10125. 2015.
- Forterre P. The common ancestor of archaea and eukarya was not an archaeon. Archaea, Vol. 2013, 372396. 2013 / López-García P, Moreira D. Open Questions on the Origin of Eukaryotes. Trends in Ecology and Evolution. Vol. 30, Issue 11, pp. 697-708. 2015-
- Koonin EV. op. cit. 2006.
- Lane N, Martin W. The energetics of genome complexity. Nature 467, 929–934. 2010.
- Koonin EV. Energetics and population genetics at the root of eukaryotic cellular and genomic complexity. Proceeding of the National Academy of Sciences of the USA. Vol. 112, no. 52, pp. 15 777-15 778. 2015.
- Lynch M. The frailty of adaptive hypotheses for the origins of organismal complexity. Proceeding of the National Academy of Sciences of the USA. Vol. 104, (Suppl. 1), 8597–8604. 2007 / Lynch M. The origins of genome archiecture. Sinauer Associates. Sunderland, MA, 2007 / Lynch M, Conery JS. The origins of genome complexity. Science 302, 1401–1404. 2003.
- . Sorprendentemente, uno dei componenti proteici centrali dello spliceosoma, Prp893Prp8 si riferisce sia alla proteina Prp8 che al gene Prp8. Il nome di Prp8 proviene da suo coinvolgimento nella lavorazione di pre-mRNA. La proteina Prp8 è una grande, altamente conservata, e unica proteina che risiede nel nucleo catalitico della spliceosoma ed è stata trovata per avere un ruolo centrale in riarrangiamenti molecolari che in questo nucleo si verifica. La proteina Prp8 è un importante componente centrale del nucleo catalitico nella spliceosoma responsabile dello splicing dell’mRNA precursore che contiene introni ed esoni. Introni inespressi vengono rimossi dal complesso spliceosoma al fine di creare una trascrizione mRNA più concisa. Lo splicing è solo una delle tante modificazioni post-trascrizionali differenti che l’mRNA deve subire prima della traduzione. La pPrp8 è stata ipotizzata anche per essere un cofattore nella catalisi di RNA.
- Dlakic M, Mushegian A. Prp8, the pivotal protein of the spliceosomal catalytic center, evolved from a retroelement-encoded reverse transcriptase. RNA 17 (5), 799–808. 2011.
- In genetica, si definiscono elementi trasponibili (chiamati anche elementi genetici mobili; in inglese MGE – Mobile genetic elements) dei segmenti di DNA capaci di spostarsi e inserirsi in diverse posizioni del genoma, tramite un meccanismo chiamato trasposizione. Scoperti la prima volta negli anni cinquanta, sono oggetto di interesse scientifico per la loro capacità di provocare mutazioni genetiche, a causa dei loro spostamenti casuali nel genoma. Sono presenti nei genomi sia procariotici che eucariotici. Esistono diversi tipi di elementi trasponibili, classificati in base alla struttura e ai meccanismi di trasposizione. Gli elementi trasponibili a oggi noti sono:trasposoni, retatrasposoni, plasmidi, elementi di DNA o RNA di virus e retrovirus, profagi, introni del gruppo II. (wikipedia) Si definiscono trasposoni alcuni elementi genetici presenti nei genomi di procarioti ed eucarioti, capaci di spostarsi da una posizione all’altra del genoma. (wikipedia).
- Meccanismo cellulare di sorveglianza di mRNA per scoprire mutazioni nonsenso e prevenire l’espressione di proteine tronche o erronee.
- L’ubiquitina è una piccola proteina regolatoria, ubiquitaria negli eucarioti. Con il termine di ubiquitinazione ci si riferisce alla modificazione post-traduzionale di una proteina dovuta al legame covalente di uno o più monomeri di ubiquitina. Tale legame porta, solitamente, alla degradazione della proteina stessa.
- Koonin EV. The origin of introns and their role in eukaryogenesis: a compromise solution to the introns-early versus introns-late debate? Biology Direct 1, 22. 2006.
- Lo splicing, ricordiamo, è una modifica del nascente pre-mRNA che avviene insieme o dopo la trascrizione, nella quale gli introni sono rimossi e gli esoni vengono uniti.
- Ibidem
- de Lange T. A loopy view of telomere evolution. Frontiers in Genetics 6, 321. October 20, 2015.
- I telomeri sono le parti finali dei cromosomi eucariotici, sono formati da sequenze oligomeriche ripetute. La necessità di queste strutture terminali è palese se si considera che tutte le DNA polimerasi conosciute duplicano le catene di DNA dall’estremità 3’ e che tutte richiedono un primer a RNA o (solo per certe DNA-polimerasi eucariotiche) a DNA. Quando la forcella di replicazione si avvicina all’estremità del cromosoma lineare, la sintesi del filamento guida continua regolarmente sino alla fine della catena stampo del DNA; la doppia elica figlia è rilasciata dopo essere stata duplicata interamente.
- Gladyshev EA, Arkhipova IR. A widespread class of reverse transcriptase-related cellular genes. Proceedings of the National Academy of Sciences of the USA 108 (51): 20311-20316. 2011.
- In tema di origine della vita, un articolo pubblicato sulla rivista “NATURE” descrive una ricerca che ha indagato su un momento chiave dell’evoluzione, quando le cellule hanno acquisito i mitocondri, organelli presenti nelle cellule di tutti gli organismi eucarioti, le più complesse tra quelle esistenti negli esseri viventi. I mitocondri hanno il loro DNA, che contiene un numero di geni variabile a seconda della specie, proprio come il DNA del nucleo cellulare ( negli esseri umani vengono ereditati per via matrilineare perché quelli degli spermatozoi vengono distrutt)i. Il DNA dei mitocondri è autonomo e ha alcune caratteristiche diverse da quello nucleare. Queste caratteristiche e altre similitudini con i batteri sono state viste come indicazioni che questi organelli si sono evoluti come organismi autonomi per poi essere inglobati nelle cellule. Una ricerca pubblicata nel 2011 sulla rivista NATURE ha mostrato prove di un comune antenato tra mitocondri e batteri della clade R11, parte della classe Alpha proteobacteria. La presenza di mitocondri ha dato un vantaggio evolutivo agli eucarioti che costituiscono la forma di vita più complessa sulla Terra. La teoria della simbiosi che ha portato ad inglobare i mitocondri raccoglie il consenso degli scienziati ma non è chiaro come ciò sia avvenuto.
- La meiosi è un processo di divisione mediante il quale una cellula eucariota con corredo cromosomico diploide dà origine a quattro cellule con corredo cromosomico aploide. Da una cellula madre si formano quattro cellule figlie, tutte diverse fra loro. Tale processo potrebbe sembrare molto simile alla mitosi ma, al contrario di questa, si ha la riduzione del corredo cromosomico in doppia copia a corredo a singola copia. Tramite poi il cosiddetto crossing-over (incrocio esterno), si ha lo scambio e la ricombinazione genetica dei cromosomi, uno dei principali eventi alla base dell’evoluzione degli organismi eucarioti. La meiosi è fondamentale nella riproduzione sessuale, la ricombinazione dell’informazione genetica proveniente dalle cellule di due individui differenti (maschio e femmina) della stessa specie, produce risultati ogni volta diversi, e naturalmente diversi anche dai due genitori. Ogni genitore fornisce un corredo cromosomico “semplice” aploide (detto anche “dimezzato”), cellula uovo nella femmina e spermatozoo nel maschio; la fusione (fecondazione) dei due corredi dimezzati (materno e paterno) e “rimescolati” ricostituisce il corredo intero e dà origine ad una singola nuova cellula, detta zigote, che diverrà il nuovo individuo.
- Ramesh MA, Malik SB, Logsdon Jr JM. A phylogenomic inventory of meiotic genes; evidence for sex in Giardia and an early eukaryotic origin of meiosis. Current Biology. 15 (2): 185-191. 2005 / Goodenough U, Heitman J. Origins of eukaryotic sexual reproduction. Cold Spring Harbor Perspectives in Biology 6, a016154. 2014 / Speijer D, Lukes J, Elias M. Sex is a ubiquitous, ancient, and inherent attribute of eukaryotic life. Proceedings of the National Academy of Sciences of the USA. Vol. 112, no. 29, 8827-8834. 2015.
- In biologia evolutiva, per ingranaggio di Muller (Muller’s ratchet) si intende il meccanismo evolutivo, ipotizzato da Hermann Joseph Muller, mediante il quale nel genoma di una popolazione che si riproduce in maniera asessuata si accumulano mutazioni deleterie in maniera irreversibile. Muller ipotizza che la riproduzione asessuata comporti una perdita di informazione genica, con conseguente perdita di intere linee di discendenza che, all’estremo, potrebbe portare anche al fenomeno dell’estinzione della popolazione. L’autore considera quindi che il sesso possa essere sorto come espediente evolutivo finalizzato a far fronte proprio a questa possibilità. Tuttavia alcuni phyla, come i rotiferi bdelloidei, sembrano essersi affidati quasi esclusivamente alla riproduzione asessuale per quasi 40 milioni di anni.
- Con il termine mutational meltdown (fusione di mutazione) ci si riferisce al processo con il quale una piccola popolazione accumula mutazioni dannose che portano a perdita della salute e al declino della grandezza della popolazione, che possono condurre ad ulteriori accumuli di mutazioni dannose per la depressione endogama. Una popolazione che si trova in questo stato è intrappolata in una spirale discendente e si estinguerà se il fenomeno si prolunga per parecchio tempo. Di solito le mutazioni dannose vengono semplicemente eliminate dalla selezione, ma durante questo processo il numero di individui che soffre di morte precoce è così grande in proporzione alla grandezza totale della popolazione che il tasso di mortalità supera quello di natalità.
- Bernstein H, Byerly HC, Hope FA, Michod RE. The evolutionary role of recombinational repair and sex. International Review of Cytology. 96, 1-28. 1985 / Kondrashov AS. Deleterious mutations and the evolution of sexual reproduction. Nature 336, 435-440. 1988 / Kondrashov AS. Sex and U. Trends in Genetics. 17 (2): 75-77. 2001.
- Takeuchi N, Kaneko K, Koonin EV. Horizontal gene transfer can rescue prokaryotes from Muller’s ratchet: benefit of DNA from dead cells and population subdivision. G3 (Bethesda) 4 (2): 325-339. 2014.
- Speijer D, Lukes J, Elias M. op. cit. 2015.
- Hickey DA. Evolutionary dynamics of transposable elements in prokaryotes and eukaryotes. Genetica 86 (1-3), 269-274. 1992 / Hickey DA. Molecular symbionts and the evolution of sex. The Journal of Heredity. 84 (5): 410-414. 1993.
- Agenti quali radiazioni o le tossine ambientali possono causare la rottura della doppia elica del DNA genomico, facilitando lo sviluppo dei tumori o di malattie neurodegenerative, di telangiectasia (AT), di atassia, di disordini e ATLD. Quindi i meccanismi efficienti della riparazione sono essenziali per la sopravvivenza e la funzione delle cellule. Il cosiddetto complesso di MRN è una componente importante di un tale sistema. Il complesso di MRN consiste della nucleasi Mre11, dell’Atpasi Rad50 e della proteina Nbs1. Nbs1 è responsabile del reclutamento del BANCOMAT della proteina, che svolge un ruolo centrale nelle fasi iniziali della risposta cellulare al danno del DNA, al sito di danno. “Come il complesso di MRN realmente riconosce le rotture a doppia elica non è ancora chiaro, Hopfner.
- La riparazione del DNA è un processo che opera costantemente nelle cellule; essa è essenziale alla sopravvivenza in quanto protegge il genoma da danni e mutazioni nocive. Nelle cellule umane, sia le normali attività metaboliche che i fattori ambientali (quali i raggi UV) possono causare danno al DNA, determinando almeno 500000 singole lesioni molecolari per cellula al giorno. Tali lesioni provocano danno strutturale alla molecola di DNA, e possono alterare in maniera drammatica il modo in cui la cellula legge le informazioni contenute nei suoi geni. Di conseguenza, il processo di riparazione del DNA deve lavorare in continuazione, per correggere qualsiasi danno nella struttura del DNA. Quando la cellula invecchia, tuttavia, la velocità di riparazione del DNA decresce fino a che non può tenere più il passo con la creazione del danno al DNA. A quel punto la cellula va incontro ad uno dei tre possibili destini: 1. Uno stato di dormienza irreversibile, detto senescenza. 2. Il suicidio della cellula chiamato apoptosi o morte cellulare programmata. 3. La carcinogenesi, ossia la formazione del cancro. La maggior parte delle cellule del corpo diviene inizialmente senescente. Poi, dopo un danno irreparabile al DNA, va incontro ad apoptosi. In tal caso, l’apoptosi rappresenta un meccanismo di ultima istanza per prevenire la trasformazione carcinogenica di una cellula, pericolosa per l’organismo. Quando le cellule divengono senescenti, le alterazioni nella biosintesi e nel turnover determinano una minore efficienza nel loro funzionamento, causando inevitabilmente malattia. La capacità di riparazione del DNA in una cellula è vitale per l’integrità del suo genoma e quindi per il normale funzionamento della cellula stessa e di tutto l’organismo. Molti geni, originariamente ritenuti capaci di influenzare la durata della vita, si sono dimostrati coinvolti nella riparazione e nella protezione dal danno al DNA.
- Operone (o operon) In genetica, gruppo di geni strutturali adiacenti, che sono trascritti tutti in una singola molecola di RNAm e che sono pertanto soggetti a una regolazione coordinata. In Escherichia coli, i geni che codificano proteine coinvolte nello stesso processo metabolico o i geni che specificano funzioni strettamente correlate, sono regolati in modo coordinato ossia sono attivati, disattivati o modulati finemente da un unico evento regolativo. Spesso i geni regolati in questo modo sono tra loro associati nel genoma e sono trascritti in una unica molecola di RNA a partire dal promotore all’estremo 5′ di tutto il gruppo di geni. L’RNA trascritto viene definito policistronico e l’insieme dei geni espressi coordinatamente prende il nome di operone. http://www.treccani.it/enciclopedia/operone Gli operoni sono comuni alla maggior parte dei procarioti, ma sono raramente trovati negli eucarioti (nematoda e pochi altri), che possiedono meccanismi di regolazione diversi. Gli operoni vennero studiati per la prima volta nel 1961 dai biologi francesi François Jacob e Jacques Monod.
- Iyer LM, Makarova KS, Koonin EV, Aravind L. Comparative genomics of the FtsK–HerA superfamily of pumping ATPases: implications for the origins of chromosome segregation, cell division and viral capsid packaging. Nucleic Acids Research. 32 (17): 5260-5279. 2004.
- Szathmáry E. Toward major evolutionary transitions theory 2.0. Proceedings of the National Academy of Sciences of the USA Vol. 112, no. 33: 10104–10111. 2015.
- I cianobatteri chiamati un tempo, ora impropriamente, anche alghe azzurre, alghe verdi-azzurre o cianoficee, sono un phylum di batteri fotosintetici. Sono organismi unicellulari procarioti, fotoautotrofi, e costituiscono uno dei 23 phyla del regno dei Bacteria.
- L’endosimbiosi è la relazione biologica definita dalla teoria endosimbiotica (anche chiamata teoria endosimbiontica o teoria dell’endosimbionte) che riguarda le origini di alcuni organismi. L’ipotesi è che alcuni organismi biologici furono ingeriti da altri organismi e poiché ne trassero un vantaggio evoluzionistico di sopravvivenza reciproco, svilupparono una relazione simbiotica permanente che nelle generazioni è divenuta indissolubile e imprescindibile.
- Ruiz-Trillo I, Burger G, Holland PWH, King N, Lang BF, Roger AJ, Gray MW. The origins of multicellularity: a multi-taxon genome initiative. Trends in Genetics. 23 (3): 113-118. 2007 / Rokas A. The molecular origins of multicellular transitions. Current Opinion in Genetics and Development. 18 (6): 472-478. 2008 / Michod RE. Evolution of individuality during the transition from unicellular to multicellular life. Proceedings of the National Academy of Sciences of the USA. 104 (Suppl. 1), 8613-8618. 2007 / Niklas KJ, Newman SA. The origins of multicellular organisms. Evolution and Development. 15 (1): 41-52. 2013 / Umen JG. Green algae and the origins of multicellularity in the plant kingdom. Cold Spring Harbor Perspectives in Biology. 6 (11): a016170. 2014 / Maliet O, Shelton DE, Michod RE. A model for the origin of group reproduction during the evolutionary transition to multicellularity. Biology Letters. 11 (6): 20150157. 2015.
- Brown MW, Kolisko M, Silberman JD, Roger AJ. Aggregative multicellularity evolved independently in the eukaryotic supergroup Rhizaria. Current Biology. 22 (12): 1123-1127. 2012 / Du Q, Kawabe Y, Schilde C, Chen Z-H, Schaap P. The evolution of aggregative multicellularity and cell–cell communication in the Dictyostelia. Journal of Molecular Biology. 427 (23): 3722-3733. 2015.
- Gli Attinomiceti (Actinobacteria) sono un raggruppamento di batteri Gram positivi. Sono filamentosi e hanno una crescita di tipo miceliare. Il loro ciclo vitale si compone di 2 parti: (1) Crescita di tipo miceliare, con il micelio infisso nel terreno. Questi tipi di attinomiceti non producono spore. (2) Riproduzione con la formazione di spore. Si verifica quando iniziano a mancare i nutrienti. Esistono alcuni tipi di attinomiceti che possiedono un micelio aereo e producono delle spore unicellulari chiamate Conidi che si trovano alle estremità delle ife. Questi conidi possono essere singoli o raggruppati in catenelle. In genere gli attinomiceti sono infissi nel terreno e, pertanto, non possiedono motilità. Alcuni tipi possono avere flagelli e muoversi. La parete cellulare è molto diversa a seconda dei tipi di attinomiceti. Oggi se ne conoscono circa 60 tipi diversi in base alla costituzione diversa della mureina della parete cellulare batterica. Hanno la capacità di attaccare composti organici di bassa biodegradabilità, come idrocarburi, lignina, humus e diversi fitofarmaci. Gli Attinomiceti filamentosi sono in grado di sprigionare nel terreno un composto chiamato geosmina, una sostanza dall’odore molto caratteristico.
- Kaiser D. Building a multicellular organism. Annual Review of Genetics. 35, 103–123. 2001 / Schirrmeister BE, Antonelli A, Bagheri HC. The origin of multicellularity in cyanobacteria. BMC Evolutionary Biology. 11, 45. 2011 / Kaiser D. Are Myxobacteria intelligent? Frontiers in Microbiology. Vol. 4, 335. 2013.
- Il quorum sensing è un sistema di regolazione trascrizionale dipendente dalla densità cellulare, ovvero un meccanismo che molte cellule batteriche della stessa specie utilizzano per comunicare tra di loro.
- Miller MB, Bassler BL. Quorum sensing in bacteria. Annual Review of Microbiology. 55, 165–199. 2001 Boyer M, Wisniewski-Dye´ F. Cell-cell signaling in bacteria: not simply a matter of quorum. FEMS Microbiology Ecology. 70 (1): 1-19. 2009.
- In biologia, il termine apoptosi (coniato nel 1972 da John F. Kerr, Andrew H. Wyllie e A. R. Currie a partire dal termine greco che indica la caduta delle foglie e dei petali dei fiori) indica una forma di morte cellulare programmata, termine con il quale il processo è stato tradizionalmente chiamato. Si tratta di un processo ben distinto rispetto alla necrosi cellulare, e in condizioni normali contribuisce al mantenimento del numero di cellule di un sistema. Di fatto negli ultimi anni si sono identificati svariati meccanismi di morte con caratteristiche più o meno simili ora all’apoptosi, ora alla necrosi. Oggi la maggior parte degli autori è concorde nel definire l’apoptosi come un meccanismo di morte cellulare programmata che presenti coinvolgimento delle caspasi.
- Leist M, Jäättelä M. Four deaths and a funeral: from caspases to alternative mechanisms. Nature Reviews. Molecular Cell Biology 2 (8): 589-598. 2001 / Baehrecke EH. How death shapes life during development. Nature Reviews. Molecular Cell Biology 3 (10): 779-787. 2002 / Ameisen JC. On the origin, evolution, and nature of programmed cell death: a timeline of four billion years. Cell Death and Differentiation. 9 (4): 367–393. 2002 / Ameisen JC. Looking for death at the core of life in the light of evolution. Cell Death Differentiation. Vol. 11 no. 1: 4-10. 2004 / Twomey C, McCarthy JV. Pathways of apoptosis and importance in development. Journal of Cellular and Molecular Medicine. 9 (2): 345-359. 2005.
- Nedelcu AM, Driscoll WW, Durand PM, Herron MD, Rashidi A. On the paradigm of altruistic suicide in the unicellular world. Evolution, international Journal of organic evolution. 65 (1): 3-20. 2011 / Taylor-Brown E, Hurd H. The first suicides: a legacy inherited by parasitic protozoans from prokaryote ancestors. Parasites & Vectors 6, 108. 2013 / Proto WR, Coombs GH, Mottram JC. Cell death in parasitic protozoa: regulated or incidental? Nature Reviews. Microbiology. 11 (1): 58-66. 2013.
- In biologia cellulare, inibizione da contatto è il comportamento di evitamento esibito da cellule simili a fibroblasti quando si trovano in contatto le une con le altre. Nella maggior parte dei casi, quando due cellule sono in contatto tra di loro, tentano di alterare la loro locomozione in una direzione diversa per evitare collisioni future. Quando la collisione è inevitabile, un fenomeno diverso avviene per cui la crescita stessa delle cellule della coltura si ferma.
- Iranzo J, Lobkovsky AE, Wolf YI, Koonin EV. Virus-host arms race at the joint origin of multicellularity and programmed cell death. Cell Cycle 13 (19): 3083-3088. 2014.
- Bourke AF. Hamilton’s rule and the causes of social evolution. Philosophical Transactions of the Royal Society of London. Series B Biological Sciences. 369, 20130362. 2014
- Gilbert OM, Foster KR, Mehdiabadi NJ, Strassmann JE, Queller DC. High relatedness maintains multicellular cooperation in a social amoeba by controlling cheater mutants. Proc. Natl Acad. Sci. USA 104, 8913–8917. 2007 Kuzdzal-Fick JJ, Fox SA, Strassmann JE, Queller DC. High relatedness is necessary and sufficient to maintain multicellularity in Dictyostelium. Science 334, 1548–1551. 2011 / Ho H-I, Hirose S, Kuspa A, Shaulsky G. Kin recognition protects cooperators against cheaters. Current Biology. 23, 1590–1595. 2013.
- Gerdes K, Christensen SK, Lobner-Olesen A. Prokaryotic toxin-antitoxin stress response loci. Nature Reviews. Microbiology. 3 (5): 371-382. 2005 / Makarova KS, Wolf YI, Koonin EV. Comprehensive comparative-genomic analysis of Type 2 toxin-antitoxin systems and related mobile stress response systems in prokaryotes. Biology Direct 4, 19. 2009 / Van Melderen L, Saavedra De Bast M. Bacterial toxin-antitoxin systems: more than selfish entities? PLoS Genetics. 5 (3): e1000437. 2009 / Leplae R, Geeraerts D, Hallez R, Guglielmini J, Drèze P, Van Melderen L. Diversity of bacterial type II toxin-antitoxin systems: a comprehensive search and functional analysis of novel families. Nucleic Acids Research. 39 (13): 5513-5525. 2011
- Un possibile modello per il fenotipo GASP ( Growth Advantage in Stationary Phase): i sistemi TA (tossina/antitossina. Un esempio di sistema plasmidico di tossina/ antitossina: parD (kis/kid). Tossina: proteina stabile (basso livello di trascrizione) Antitossina: proteina instabile (livello di trascrizione + alto) I sistemi TA si ritrovano frequentemente su plasmidi ed elementi mobili, con l’unica apparente funzione di eliminare i microrganismi (ricombinanti, segreganti ecc.) che non ne mantenessero la sequenza codificante (cosiddetto “selfish DNA”).
- Guglielmini J, Van Melderen L. Bacterial toxinantitoxin systems: Translation inhibitors everywhere. Mobile Genetic Elements. 1 (4): 283-290. 2011 / Rankin DJ, Turner LA, Heinemann JA, Brown SP. The coevolution of toxin and antitoxin genes drives the dynamics of bacterial addiction complexes and intragenomic conflict. Proceedings. Biological Sciences. 279, 3706-3715. 2012 152. Mochizuki A, Yahara K, Kobayashi I, Iwasa Y. Genetic addiction: selfish gene’s strategy for symbiosis in the genome. Genetics 172 (2): 1309-1323. 2006.
- Iranzo J, Lobkovsky AE, Wolf YI, Koonin EV. op. cit. 2014.
- La Sonic Hedgehog Homolog (SHH) è una delle tre proteine della famiglia delle hedgehog; le altre due sono la Desert Hedgehog (DHH) e la Indian Hedgehog (IHH). SHH è uno dei ligandi più studiati della Via di segnalazione del hedgehog (Hedgehog signaling pathway); questa via è fondamentale nella regolazione dell’organogenesi nei vertebrati, per esempio nel differenziamento delle dita e degli arti, nell’organizzazione del sistema nervoso e dei denti. La Sonic Hedgehog è il migliore esempio di molecola morfogenetica: tale molecola si diffonde producendo un gradiente di concentrazione, e le cellule dell’embrione si sviluppano in tessuti diversi, a seconda della concentrazione locale di SHH. Ma tale molecola è importante anche nell’età adulta: controlla la divisione cellulare delle cellule staminali adulte ed è implicata in alcuni tipi di cancro. wikipedia.
- Un’inteina è un segmento di una proteina che è in grado di asportare se stessa e unire le porzioni restanti (exteins) con un legame peptidico in un processo chiamato splicing della proteina.
- Naito T, Kusano K, Kobayashi I. Selfish behavior of restriction-modification systems. Science 267, 897–899. 1995 / Kobayashi I. Behavior of restriction–modification systems as selfish mobile elements and their impact on genome evolution. Nucleic Acids Research. 29, 3742–3756. 2001 / Van Melderen L. Toxin–antitoxin systems: why so many, what for? Current Opinion. Microbiology. 13, 781–785. 2010 / Makarova KS, Wolf YI, Koonin EV. Comparative genomics of defense systems in archaea and bacteria. Nucleic Acids Research. 41, 4360–4377. 2013.
- Il sistema di modifica della restrizione (sistema RM) viene utilizzato da batteri e, forse, da altri organismi procarioti per proteggersi dal DNA estraneo, come quella a trasportato da batteriofagi.
- Mochizuki A, Yahara K, Kobayashi I, Iwasa Y. op. cit. 2006.
- Gerdes K, Christensen SK, Lobner-Olesen A. op. cit. 2005 / Van Melderen L, Saavedra De Bast M. op. cit. 2009 Van Melderen L. op. cit. 2010.
- L’interfase è il periodo di tempo del ciclo di divisione cellulare delle cellule eucariotiche che intercorre tra una mitosi e quella successiva. In tale periodo avviene il processo di duplicazione del materiale genetico (DNA) e di alcuni organelli cellulari, quali i centrioli ed i mitocondri, ed in generale l’aumento di massa e di dimensioni della cellula, in modo tale da permettere la formazione di due cellule figlie a partire dalla cellula madre.
- Le ribonucleasi, abbreviate comunemente RNasi, sono delle nucleasi che catalizzano l’idrolisi dell’acido ribonucleico (RNA) che viene così scisso in componenti più piccoli.
- Christensen-Dalsgaard M, Overgaard M, Winther KS, Gerdes K. 2008 RNA decay by messenger RNA interferases. Methods in Enzymology. 447, 521-535 / Cook GM, Robson JR, Frampton RA, McKenzie J, Przybilski R, Fineran PC, Arcus VL. Ribonucleases in bacterial toxin-antitoxin systems. Biochimica et Biophysica Acta. 1829 (6-7): 523-531. 2013.
- Nucleotidyltransferases sono enzimi transferasi di gruppi contenenti fosforo, per esempio, sostituenti di acidi nucleotidylic o semplicemente monofosfati. Transferasi Nucleotidyl è un componente del percorso per la riparazione del singolo nucleotide basato sull’escissione. Questo meccanismo di riparazione inizia quando un singolo nucleotide è riconosciuto da DNA glicosilasi come erroneamente abbinato o è stato mutato in qualche modo (luce UV, mutageno chimico, ecc), e viene rimosso. Più tardi, un tranferase nucleotidyl viene utilizzato per colmare il divario con la base corretta, utilizzando il filamento come modello di riferimento.
- Dy RL, Przybilski R, Semeijn K, Salmond GP, Fineran PC. A widespread bacteriophage abortive infection system functions through a Type IV toxin–antitoxin mechanism. Nucleic Acids Research. 42, 4590-4605. 2014.
- Bickle TA, Kruger DH. Biology of DNA restriction. Microbiological Reviews. 57 (2): 434-450. 1993 / Vasu K, Nagaraja V. Diverse functions of restriction-modification systems in addition to cellular defense. Microbiology and Molecular Biology Reviews. 77 (1): 53-72. 2013.
- Le endonucleasi sono enzimi idrolitici, identificati negli anni settanta, che scindono il legame fosfodiesterico all’interno di una catena polinucleotidica, dividendola in due polimeri, a differenza delle esonucleasi che ne distaccano il nucleotide terminale. Endonucleasi sono coinvolte nella riparazione del DNA e nella maturazione dell’RNA degli Eucarioti.
- DAM metilasi, abbreviazione di Deoxy/adenosine/methylase, è un enzima che aggiunge un gruppo metilico all’adenina della sequenza 5’-GATC-3’ nel DNA di nuova sintesi. Subito dopo la sintesi del DNA, la figlia strand rimane non-metilata per un breve periodo. Ruolo nel mismatch repair del DNA: quando il DNA polimerasi fa un errore risultante in un mismatched base-pair o in una piccolo inserimento o eliminazione durante la sintesi del DNA, la cellula riparerà il DNA attraverso un percorso chiamato mismatch repair. Tuttavia, la cella deve essere in grado di distinguere tra il filamento stampo e il filamento di nuova sintesi. Nei batteri, filamenti di DNA sono metilati da Dam metilasi e quindi, immediatamente dopo la replicazione, il DNA sarà hemi-metilato.
- Naito Y, Naito T, Kobayashi I. Selfish restriction modification genes: resistance of a resident R/M plasmid to displacement by an incompatible plasmid mediated by host killing. Biological Chemistry. 379 (4-5): 429-436. 1998 / Handa N, Kobayashi I. Post-segregational killing by restriction modification gene complexes: observations of individual cell deaths. Biochimie 81 (8-9): 931-938. 1999.
- Il sistema hok/sok (dall’inglese: host killing/supressor of killing, uccisione dell’ospite, soppressione dell’uccisione), è, in biologia molecolare un sistema di selezione post-segregazionale del plasmide R1 di Escherichia coli. Il sistema è controllato dai due geni hok e sok: il prodotto dei due geni può essere considerato rispettivamente come un veleno a lunga vita ed un antidoto a breve vita. Dopo la divisione cellulare se una delle cellule figlie non contiene il plasmide, essa non produrrà più l’antidoto e morirà, visto che il veleno ha una vita più lunga dell’antitodo. Invece cellule contenenti il plasmide continueranno a produrre l’antidoto e potranno sopravvivere: il sistema viene detto postsegregazionale appunto perché la morte cellulare avviene dopo la segregazione del plasmide. Il gene hok codifica per una proteina citotossica di 52 amminoacidi, che causa morte cellulare per depolarizzazione della membrana. Il processo di traduzione dell’mRNA di hok è però inibito dal trascritto del gene sok, che agisce come regolatore antisenso: questi lega l’mRNA di hok e forma un duplex riconosciuto e degradato dalla RNAsi III. Il meccanismo di selezione è ottenuto tramite le differenti velocità di degradazione dei due trascritti: l’mRNA di hok è abbastanza stabile, mentre il trascritto antisenso di sok viene rapidamente degradato, il che permetterebbe l’espressione di hok, se non che il livello di espressione di sok è molto più elevato di quello di hok, compensando per la minor stabilità. In questo modo hok non viene tradotto in proteina nelle cellule contenenti il plasmide, però la perdita del plasmide causa uno sbilancio tra il trascritto di hok, stabile e quello di sok, rapidamente degradato, portando alla sintesi della proteina hok e infine a morte cellulare. Wiki.
- CRISPR (clustered regularly interspaced short palindromic repeats, [brevi ripetizioni palindrome raggruppate e separate a intervalli regolari) è il nome attribuito a segmenti di DNA contenenti brevi sequenze ripetute, scoperti all’interno di cellule procariote (in passato, la terminologia era Short Regularly Spaced Repeats, abbreviato in SRSR). Ogni ripetizione è seguita da brevi frammenti di DNA “distanziatore” generato da una passata esposizione del batterio a virus batteriofagi o plasmidi. Le sequenze CRISPR sono state rinvenute in circa il 40% dei genomi batterici e nel 90% dei genomi degli Archea sottoposti a sequenziamento. La funzione biologica e l’importanza delle CRISPR sono state rivelate dalla scoperta dell’esistenza di un complesso di geni associati a tali sequenze, denominato Cas (contrazione di CRISPR-associated), in grado di codificare per presunte proteine di nucleasi ed elicasi, che sono enzimi in grado di tagliare il DNA. In questo modo, l’associazione CRISPR/Cas costituisce un sistema immunitario procariotico che conferisce resistenza nei confronti di elementi genetici estranei come plasmidi e fagi e provvede, quindi, a una sorta di immunità acquisita. Le sequenze “distanziatrici” dei CRISPR riconoscono e tagliano questi elementi estranei con un meccanismo analogo alla RNA interference degli organismi eucaristici
- Shah SA, Garrett RA. CRISPR/Cas and Cmr modules, mobility and evolution of adaptive immune systems. Research in Microbiology. 162 (1): 27-38. 2011 / Makarova KS et al. An updated evolutionary classification of CRISPR-Cas systems. Nature Reviews. Microbiology. 13 (11): 722-736. 2015.
- Krupovic M, Makarova KS, Forterre P, Prangishvili D, Koonin EV. Casposons: a new superfamily of self-synthesizing DNA transposons at the origin of prokaryotic CRISPR- Cas immunity. BMC Biology. 12: 36. 2014.
- Koonin EV, Krupovic M. Evolution of adaptive immunity from transposable elements combined with innate immune systems. Nature Reviews. Genetics. 16 (3): 184-192. 2015.
- Nunez JK, Lee AS, Engelman A, Doudna JA. Integrase-mediated spacer acquisition during CRISPR-Cas adaptive immunity. Nature 519, 193–198. 2015.
- Noto T, Kataoka K, Suhren JH, Hayashi A, Woolcock KJ, Gorovsky MA, Mochizuki K. Small-RNAmediated genome-wide trans-recognition network in tetrahymena DNA elimination. Molecular Cell 59 (2): 229-242. 2015.
- In biochimica, una molecola effettrice è di solito una piccola molecola che si lega selettivamente ad una proteina e regola la sua attività biologica. In questo modo, le molecole effettrici agiscono come leganti che possono aumentare o diminuire l’attività enzimatica, l’espressione genica o la segnalazione cellulare. Le molecole effettrici possono, anche, regolare direttamente l’attività di alcune molecole di mRNA (riboswitches).
- Shmakov S et al. Discovery and functional characterization of diverse class 2 CRISPR-Cas systems. Molecular Cell 60 (3): 385-397. 2015.
- Koonin EV, Krupovic M. A movable defense. The Scientist. 2015.
- Seed KD, Lazinski DW, Calderwood SB, Camilli A. A bacteriophage encodes its own CRISPR/Cas adaptive response to evade host innate immunity. Nature 494, 489–491. 2013.
- Koonin EV. 2014 The double-edged sword of Lamarck: comment on ‘Diversity, evolution, and therapeutic applications of small RNAs in prokaryotic and eukaryotic immune systems’ by Edwin L. Cooper and Nicola Overstreet. Physics of Life Reviews. 11 (1): 141-143; discussion 149–151.
- (La cromatina è la forma in cui gli acidi nucleici si trovano nella cellula e consiste in un sistema di impacchettamento, ad esempio, per i quasi due 2m di DNA genomico umano nel ristretto spazio nucleare. La cromatina presiede a molti fondamentali processi).
- Aravind L, Anantharaman V, Zhang D, de Souza RF, Iyer LM. Gene flow and biological conflict systems in the origin and evolution of eukaryotes. Frontiers in Cell Infection and Microbiology. 2, 89. 2012.
- Szathmáry E. Toward major evolutionary transitions theory 2.0. Proceedings of the National Academy of Sciences of the USA Vol. 112, no. 33: 10104–10111. 2015.
- Toro N, Nisa-Martinez R. Comprehensive phylogenetic analysis of bacterial reverse transcriptases. PLoS ONE 9 (11): e114083. 2014 / Schmitz-Linneweber C, Lampe MK, Sultan LD, Ostersetzer-Biran O. Organellar maturases: A window into the evolution of the spliceosome. Biochimica et Biophysica Acta. 1847 (9): 798-808. 2015.
- Basu MK, Rogozin IB, Deusch O, Dagan T, Martin W, Koonin EV. Evolutionary dynamics of introns in plastid-derived genes in plants: saturation nearly reached but slow intron gain continues. Molecular Biology and Evolution. 25 (1): 111-119. 2008.
- Nunn CL, Craft ME, Gillespie TR, Schaller M, Kappeler PM. The sociality–health–fitness nexus: synthesis, conclusions and future directions. Philosophical Transactions of the Royal Society of London. Series B, Biological sciences. 370, 20140115. 2015 / Kappeler PM, Cremer S, Nunn CL. Sociality and health: impacts of sociality on disease susceptibility and transmission in animal and human societies. Philosophical Transactions of the Royal Society of London. Series B, Biological sciences. 370, 20140116. 2015.
- Brunet TD, Doolittle WF. Multilevel selection theory and the evolutionary functions of transposable elements. Genome Biology and Evolution. Vol. 7, Issue 8: 2445-2457. 2015.
- Kapitonov VV, Jurka J. RAG1 core and V(D)J recombination signal sequences were derived from Transib transposons. PLoS Biology 3, e181. 2005 / Kapitonov VV, Koonin EV. Evolution of the RAG1-RAG2 locus: both proteins came from the same transposon. Biology Direct 10, 20. 2015.
- Env è una proteina virale che serve per formare la busta virale. L’espressione del gene ENV permette che i retrovirus possano indirizzarsi e collegarsi a specifici tipi cellulari, e di infiltrarsi nella membrana delle cellule bersaglio.
- HERV-W_7q21.2 provirus ancestrale Env poliproteina, noto anche come sincitina o enverin, è una proteina codificata da un elemento virale endogeno. Negli esseri umani, il gene viene chiamato sincitina ERVWE1. Syncytins sono geni che codificano proteine derivate dalla proteina dell’involucro di elementi retrovirali endogeni che sono stati catturati e addomesticati in più riprese ed indipendentemente in diverse specie di mammiferi, analogamente alla incorporazione di alcune specie batteriche in cellule animali durante il corso dell’evoluzione che infine si sono sviluppati in mitocondri. Il gene knockout dei geni sincitina nei topi fornisce la prova per il loro requisito assoluto per lo sviluppo della placenta e la sopravvivenza degli embrioni.
- Dupressoir A, Lavialle C, Heidmann T. From ancestral infectious retroviruses to bona fide cellular genes: role of the captured syncytins in placentation. Placenta 33 (9): 663- 671. 2012 / Lavialle C, Cornelis G, Dupressoir A, Esnault C, Heidmann O, Vernochet C, Heidmann T. Paleovirology of ’syncytins’, retroviral envgenes exapted for a role in placentation. Philosophical Transactions of the Royal Society of London. Series B, Biological sciences 368, 20120507. 2013 / Imakawa K, Nakagawa S, Miyazawa T. Baton pass hypothesis: successive incorporation of unconserved endogenous retroviral genes for placentation during mammalian evolution. Genes Cells 20 (10): 771-788. 2015.
- McInerney JO, Pisani D, Bapteste E, O’Connell MJ. The public goods hypothesis for the evolution of life on Earth. Biology Direct 6, 41. 2011 / McInerney J, Cummins C, Haggerty L. Goods-thinking vs. tree-thinking: finding a place for mobile genetic elements. Mobile Genetic Elements 1 (4): 304-308. 2011.
- Koonin EV, Martin W. On the origin of genomes and cells within inorganic compartments. Trends in Genetics. 21 (12): 647-654. 2005.
- Archibald JM. Endosymbiosis and eukaryotic cell evolution. Current Biology. 25 (19): R911-R921. 2015 Martin WF, Garg S, Zimorski V. Endosymbiotic theories for eukaryote origin. Philosophical Transactions of the Royal Society of London. Series B, Biological sciences. 370, 20140330. 2015.
- Koonin Eugene V. Viruses and mobile elements as drivers of evolutionary transitions. Philosophical Transactions of the Royal Society B. Series Biological sciences. 371: 20150442, 2016.